グルタミンシンテターゼ
| グルタミンシンテターゼ | |||||||||
|---|---|---|---|---|---|---|---|---|---|
 ネズミチフス菌 Salmonella Typhimurium のグルタミンシンテターゼの2つのモノマーの間の活性部位。カチオン結合部位が黄色と橙色、ADPが桃色、ホスフィノスリシン (phosphinothricin) が青色で示されている[1]。 | |||||||||
| 識別子 | |||||||||
| EC番号 | 6.3.1.2 | ||||||||
| CAS登録番号 | 9023-70-5 | ||||||||
| 別名 | グルタミン合成酵素 (glutamine synthetase)、グルタミン酸-アンモニアリガーゼ (glutamate-ammonia ligase) | ||||||||
| データベース | |||||||||
| IntEnz | IntEnz view | ||||||||
| BRENDA | BRENDA entry | ||||||||
| ExPASy | NiceZyme view | ||||||||
| KEGG | KEGG entry | ||||||||
| MetaCyc | metabolic pathway | ||||||||
| PRIAM | profile | ||||||||
| PDB構造 | RCSB PDB PDBj PDBe PDBsum | ||||||||
| 遺伝子オントロジー | AmiGO / QuickGO | ||||||||
| |||||||||
| グルタミンシンテターゼ beta-Grasp ドメイン | |||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|
| 識別子 | |||||||||||
| 略号 | Gln-synt_N | ||||||||||
| Pfam | PF03951 | ||||||||||
| InterPro | IPR008147 | ||||||||||
| PROSITE | PDOC00162 | ||||||||||
| SCOP | 2gls | ||||||||||
| SUPERFAMILY | 2gls | ||||||||||
| |||||||||||
| グルタミンシンテターゼ 触媒ドメイン | |||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|
 ネズミチフス菌 Salmonella Typhimurium のグルタミンシンテターゼの12サブニット構造[2]。 | |||||||||||
| 識別子 | |||||||||||
| 略号 | Gln-synt_C | ||||||||||
| Pfam | PF00120 | ||||||||||
| Pfam clan | CL0286 | ||||||||||
| InterPro | IPR008146 | ||||||||||
| PROSITE | PDOC00162 | ||||||||||
| SCOP | 2gls | ||||||||||
| SUPERFAMILY | 2gls | ||||||||||
| |||||||||||
| グルタミン酸-アンモニアリガーゼ (グルタミンシンテターゼ) | |
|---|---|
| 識別子 | |
| 略号 | GLUL |
| 他の略号 | GLNS |
| Entrez | 2752 |
| HUGO | 4341 |
| OMIM | 138290 |
| PDB | 2qc8 (RCSB PDB PDBe PDBj) |
| RefSeq | NM_002065 |
| UniProt | P15104 |
| 他のデータ | |
| EC番号 (KEGG) | 6.3.1.2 |
| 遺伝子座 | Chr. 1 q31 |
グルタミンシンテターゼまたはグルタミン合成酵素 (グルタミンごうせいこうそ、Glutamine synthetase、GS、 EC 6.3.1.2[3]) は、窒素の代謝に必須の役割を果たす酵素で、グルタミン酸とアンモニアの縮合によってグルタミンを合成する反応を触媒する。
グルタミン酸 (Glutamate) + ATP + アンモニア (NH3) → グルタミン (Glutamine) + ADP + リン酸 (Pi)

グルタミンシンテターゼ (GS) は硝酸イオンの還元、アミノ酸の分解、光呼吸によって生じたアンモニアを利用する[4]。グルタミンのアミド基が、グルタミンを経由するの代謝産物を合成する際の窒素源となる[5]。
アンモニウムイオンと水分子の競合、それらの結合親和性、アンモニウムイオンの濃度は、グルタミンの合成と加水分解に影響を与える。アンモニウムイオンがアシル-リン酸中間体を攻撃したときにはグルタミンが形成され、水分子が攻撃したときにはグルタミン酸が再形成される[6][7]。カチオンと負に帯電したポケットの間の静電的な力のため、アンモニウムイオンは水分子よりも強くGSへ結合する[4]。他の反応としては、アンモニウムイオン (NH4+) ではなくヒドロキシルアミン (NH2OH) がGSに結合し、γ-グルタミルヒドロキサム酸 (γ-glutamylhydroxamate) が生じる反応が考えられる[6][7]。
構造[編集]

GSは、8、10、または12の同一のサブユニットから構成され、2層のリング構造が互いに向かい合って結合した形状をしている[6][8][9][10]。細菌のGSは十二量体であり、それぞれのモノマー間に計12個の活性部位が存在する[6]。各活性部位は、3つの異なる基質(ヌクレオチド、アンモニウムイオン、アミノ酸)の結合部位となる「トンネル」を形成している[4][6][10][11]。このトンネルは中央部がくびれた "bifunnel" 構造であり、bifunnelの頂部が外部への開口部となっており、そこにATPが結合する[4]。そして、グルタミン酸は底部に結合する[7]。bifunnelの中央部には、2価カチオン(マンガンイオンMn2+またはマグネシウムイオンMg2+)の結合部位が2つ存在する。1つはATPからグルタミン酸へのリン酸基の転移に関与しており、もう1つはGSの活性型構造を安定させてグルタミン酸の結合を助けている[6]。
GSの2層のリング間の結合は、水素結合と疎水的相互作用によって保たれている。各サブユニットのC末端領域 (helical thong) が、反対側のリングの向かい合ったサブユニットの疎水的領域に入り込み、GSの構造を安定化している。加えて、リングの中央部のチャネルは、リングの両側のサブユニットで形成された4枚の逆平行β-シート構造が6つ並ぶことで構成されている[6]。
機構[編集]
GSは、グルタミン酸とアンモニアのATP依存的な縮合反応によるグルタミンの合成を触媒する[4]。ATPの加水分解は、協奏的な二段階反応の1段階目を駆動する[4][6][8]。ATPはグルタミン酸をリン酸化して、ADPとアシル-リン酸中間体であるγ-グルタミルリン酸を形成し、その後に中間体がアンモニアと反応して、グルタミンと無機リン酸が形成される。ADPと無機リン酸はアンモニアが結合してグルタミンが放出されるまで解離しない[6]。
まずATPは活性部位の頂部のカチオン結合部位の近傍に結合し、一方グルタミン酸は活性部位の底部のカチオン結合部位の近傍に結合する[5][7]。ADPの存在によってGSのコンフォメーションの遷移が引き起こされ、γ-グルタミルリン酸が安定化される。この中間体が存在しているときのみ、アンモニウムイオンはGSに強く結合する。結合部位は極性的で溶媒に露出しているため、結合するのはアンモニアよりもアンモニウムイオンである[7]。反応の2段階目では、アンモニウムイオンが脱プロトン化され、アンモニアが中間体を攻撃しグルタミンが形成される[12]。リン酸は活性部位の頂部を通って移動し、グルタミンは底部(2層のリングの間)を通って放出される[7][9]。

生物学的機能[編集]
GSは主に脳、腎臓、肝臓に存在する[4][10]。脳のGSはグルタミン酸の代謝調節、アンモニアの解毒・同化、神経伝達物質によるシグナルの終結と再生に関与している[4][13]。GSは脳の中で、主にアストロサイトに見つかる[14]。アストロサイトは余剰のアンモニアとグルタミン酸を取り込み、神経を興奮毒性から保護する[13]。高アンモニア環境では、アストロサイトの腫脹が生じる[13][15][16]。ある研究では、アストロサイトの形態の変化によってグルタミン酸作動性領域の周辺でGSの発現が上昇し、高レベルのグルタミン酸とアンモニアを減少させる適応が起こることが示されている[13]。また他の研究では、アストロサイトの腫脹はグルタミンの蓄積によるものとされ、高アンモニアによる皮質組織の水分量の増加は、L-メチオニン-S-スルホキシイミンによってGSを阻害することで抑制された[15]。
分類[編集]
GSは3つの異なるクラスに分類される[17][18][19]。
- クラスIの酵素 (GSI) は原核生物に特有で、12の同一のサブユニットで構成される[20]。GSI型の酵素活性はチロシン残基のアデニリル化で制御される。アデニリル化された酵素は不活性となる[21]。
- クラスIIの酵素 (GSII) は真核生物とリゾビウム科、フランキア科、ストレプトマイセス科に属する細菌(これらの細菌にはGSIも存在する)に見つかる[10]。PDB: 2OJW
植物は2つ以上のGSIIを持っており、アイソザイムの1つは葉緑体へ移動する。他のものは細胞質に位置する。細胞質のGSの遺伝子の翻訳は5'UTRで調節されており、3'UTRは転写産物のターンオーバーに関与する[22]。
- クラスIIIの酵素 (GSIII) は、現在では Bacteroides fragilis と Butyrivibrio fibrisolvens に見つかっているのみである。同一のサブユニットから構成される二重のリングの十二量体である[23]。大きさはGSI(450–470アミノ酸)、GSII(350–420アミノ酸)よりも大きい(約700アミノ酸)。
GSの3つのクラスは明らかに構造的関連性があるが、配列類似性はあまり高くない。
調節と阻害[編集]
GSの調節は原核生物でのみ行われる[24]。GSは可逆的な共有結合修飾を受ける。12のサブユニットのチロシン残基に対し、二機能性の調節酵素であるアデニリルトランスフェラーゼ (adenylyl transferase、AT) によってアデニリル化、脱アデニリル化の双方が行われる[24]。アデニリル化は、タンパク質の側鎖にAMPを共有結合付加する翻訳後修飾である。アデニリル化にはATPを必要とし、GSの完全な阻害には12分子のATPが必要である。ATによる脱アデニリル化は、チロシン残基に結合したアデニリル基を加リン酸分解し、ADPとして解離させる。ATの活性は、ATに結合したPIIと呼ばれる44 kDaの三量体調節タンパク質の影響を受ける[24]。PIIもまたウリジリルトランスフェラーゼ (uridylyl transferase) による翻訳後修飾を受けるため、2状態が存在する。PIIがウリジリル化されていないときはPIIA型となり、AT:PIIA複合体はGSをアデニリル化し不活性化する。PIIがウリジリル化されているときはPIID型となり、AT:PIID複合体はGSを脱アデニリル化し活性化する[24]。AT:PIIA複合体とAT:PIID複合体は、α-ケトグルタル酸とグルタミンによって逆方向のアロステリックな調節を受ける。グルタミンはAT:PIIAを活性化してAT:PIIDを阻害し、アデニリル化によってGSを不活性化する。さらに、グルタミン酸はPIID型からPIIA型への変換を促進する。α-ケトグルタル酸の複合体への影響は、グルタミンの正反対である[24]。グラム陰性細菌の大部分では、GSはアデニリル化による修飾を受ける (一部のシアノバクテリアや緑藻は例外である)[25]。
GSの阻害は、大部分がアミノ酸の結合部位に集中している[6]。阻害剤としては、グルタミンの代謝の結果生じる、トリプトファン、ヒスチジン、カルバモイルリン酸、グルコサミン-6-リン酸、CTP、AMPがある[5][8][26]。また、アラニン、グリシンとセリンがGSのグルタミン酸結合部位に結合し、GDP、AMP、ADPがATP結合部位に結合する[6]。アラニン、グリシンとセリンはアデニリル化されていないGSのグルタミン酸結合部位に結合し、これら4つのアミノ酸は、それらに共通の「主鎖」の原子を利用して結合する[5]。グルタミン酸もグルタミンの代謝産物であり、グルタミン酸はGSの基質であるとともに阻害も行い、GSの調節因子として機能する。各阻害剤は酵素の活性を低下させ、グルタミンの代謝産物がすべての部位に結合すると、GSの活性はほぼ完全に阻害される[8]。阻害を行う入力シグナルが多数存在することで、体内の窒素レベルに応じたGSの繊細な調節が可能となっている。フィードバック調節には脳と他の組織で差異があり、脳以外のGSは、グルタミンやその誘導体によってフィードバック阻害を受けるが、脳のGSは阻害されない[6]。
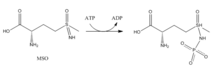
他の阻害剤としては、次のようなものがある。
- メチオニンスルホキシイミン (methionine sulfoximine、MSO)
- MSOはグルタミン酸結合部位に結合する阻害剤である。GSに結合するとMSOはATPによってリン酸化され、不可逆的な非共有結合性の阻害を行う。S体(L-メチオニン-S-スルホキシイミン)がより高い阻害効果を持つ[6]。活性部位にある柔軟なループ構造がMSOによって安定化され、グルタミン酸の活性部位への進入がブロックされる[7]。
- ホスフィノスリシン (phosphinothricin、PPT、グルホシネート、Glufosinate)
- ホスフィノスリシンはグルタミン酸結合部位に結合する阻害剤で、除草剤として用いられている。ホスフィノスリシン処理された植物は、アンモニアが蓄積し光合成が停止するため枯死する[10]。
今日では多くの合成阻害剤が利用可能である[6]。
大腸菌を用いた研究によって、GSは遺伝子発現も調節されていることが明らかにされた。GSのサブユニットをコードする遺伝子はglnAである。glnAの転写はエンハンサー領域に結合する特異的転写因子NRI (NtrC) に依存し、NRIがリン酸化型のとき転写は活性化される。NRIのリン酸化は、プロテインキナーゼであるNRII (NtrB) によって触媒される。NRIIがPIIAと複合体を形成しているときはホスファターゼとして機能し、NRIは脱リン酸化されてglnAの転写は止まる[24]。
シアノバクテリアには全く異なる調節機構が存在する[27]。上述のNtrC-NtrB二成分制御系の代わりに[28][29]、シアノバクテリアは転写調節因子NtcAを持っている。NtcAはこのクレードのみに存在し、GSや窒素代謝に関与する一群の遺伝子の発現を調節する[30][31]。さらに、シアノバクテリアのGSはフィードバック阻害の感受性を向上させるための共有結合修飾が行われない[29]。代わりに、シアノバクテリアのGSはGS不活性化因子 (GS inactivation factor、IF) と名付けられた低分子量タンパク質によって阻害され、IFの転写はNtcAによって負の制御を受けている[32][33]。これらの不活性化因子はさらにノンコーディングRNAによって調節されている。低分子RNAであるNsiR4はIF7 (gifA) のmRNAの5'UTRと相互作用し、発現を低下させる。NsiR4の発現はNtcAによって正の制御を受けている[34]。加えて、IF17の発現はグルタミンが結合するリボスイッチによって制御されている[35]。
出典[編集]
- ^ a b c PDB: 1FPY; “The crystal structure of phosphinothricin in the active site of glutamine synthetase illuminates the mechanism of enzymatic inhibition”. Biochemistry 40 (7): 1903–12. (February 2001). doi:10.1021/bi002438h. PMID 11329256.
- ^ PDB: 2GLS; “Refined atomic model of glutamine synthetase at 3.5 A resolution”. J. Biol. Chem. 264 (30): 17681–90. (October 1989). PMID 2572586.
- ^ “Some evolutionary relationships of the primary biological catalysts glutamine synthetase and RuBisCO”. Cold Spring Harb. Symp. Quant. Biol. 52: 483–90. (1987). doi:10.1101/sqb.1987.052.01.055. PMID 2900091.
- ^ a b c d e f g h “Discovery of the ammonium substrate site on glutamine synthetase, a third cation binding site”. Protein Sci. 4 (11): 2358–65. (Nov 1995). doi:10.1002/pro.5560041114. PMC 2143006. PMID 8563633.
- ^ a b c d “Feedback inhibition of fully unadenylylated glutamine synthetase from Salmonella typhimurium by glycine, alanine, and serine”. Proc. Natl. Acad. Sci. USA 90 (11): 4996–5000. (Jun 1993). doi:10.1073/pnas.90.11.4996. PMC 46640. PMID 8099447.
- ^ a b c d e f g h i j k l m n “Structure-function relationships of glutamine synthetases”. Biochim Biophys Acta 1477 (1–2): 122–45. (Mar 2000). doi:10.1016/S0167-4838(99)00270-8. PMID 10708854.
- ^ a b c d e f g “Structural model for the reaction mechanism of glutamine synthetase, based on five crystal structures of enzyme-substrate complexes”. Biochemistry 33 (3): 675–81. (Jan 1994). doi:10.1021/bi00169a007. PMID 7904828.
- ^ a b c d Biochemistry (6th ed.). San Francisco: W.H. Freeman. (2007). pp. 679–706. ISBN 0-7167-8724-5
- ^ a b Goodsell DS (2002年6月). “Glutamine Synthetase”. Molecule of the month. RCSB Protein Data Bank. 2010年5月8日閲覧。
- ^ a b c d e “Crystal structures of mammalian glutamine synthetases illustrate substrate-induced conformational changes and provide opportunities for drug and herbicide design”. J Mol Biol 375 (1): 317–28. (Jan 2008). doi:10.1016/j.jmb.2007.10.029. PMID 18005987.
- ^ “Some effects of adenylylation on the biosynthetic properties of the glutamine synthetase from Escherichia coli”. Biochemistry 9 (3): 633–49. (Feb 1970). doi:10.1021/bi00805a025. PMID 4906326.
- ^ “Metal ion requirement by glutamine synthetase of Escherichia coli in catalysis of gamma-glutamyl transfer”. Arch Biochem Biophys 166 (1): 102–24. (Jan 1975). doi:10.1016/0003-9861(75)90370-7. PMID 235885.
- ^ a b c d “Glutamine synthetase in brain: effect of ammonia”. Neurochem. Int. 41 (2–3): 123–42. (Aug–Sep 2002). doi:10.1016/S0197-0186(02)00033-5. PMID 12020613.
- ^ Venkatesh K, Srikanth L, Vengamma B, Chandrasekhar C, Sanjeevkumar A, Mouleshwara Prasad BC, Sarma PV. In vitro differentiation of cultured human CD34+ cells into astrocytes. Neurol India 2013;61:383-8
- ^ a b “Inhibition of glutamine synthetase reduces ammonia-induced astrocyte swelling in rat”. Neuroscience 71 (2): 589–99. (March 1996). doi:10.1016/0306-4522(95)00462-9. PMID 9053810.
- ^ “Effect of glutamine synthetase inhibition on astrocyte swelling and altered astroglial protein expression during hyperammonemia in rats”. Neuroscience 131 (2): 437–49. (2005). doi:10.1016/j.neuroscience.2004.10.045. PMC 1819407. PMID 15708485.
- ^ “Evolution of the glutamine synthetase gene, one of the oldest existing and functioning genes”. Proc. Natl. Acad. Sci. U.S.A. 90 (7): 3009–13. (April 1993). doi:10.1073/pnas.90.7.3009. PMC 46226. PMID 8096645.
- ^ “Glutamine synthetase II in Rhizobium: reexamination of the proposed horizontal transfer of DNA from eukaryotes to prokaryotes”. J. Mol. Evol. 29 (5): 422–8. (November 1989). doi:10.1007/BF02602912. PMID 2575672.
- ^ “Evolutionary relationships of bacterial and archaeal glutamine synthetase genes”. J. Mol. Evol. 38 (6): 566–76. (June 1994). doi:10.1007/BF00175876. PMID 7916055.
- ^ “GSI structure”. 2008年12月17日時点のオリジナルよりアーカイブ。2009年3月31日閲覧。
- ^ InterPro:IPR001637 Glutamine synthetase class-I, adenylation site
- ^ “The 5' untranslated region of the soybean cytosolic glutamine synthetase β(1) gene contains prokaryotic translation initiation signals and acts as a translational enhancer in plants”. Molecular Genetics and Genomics 287 (11–12): 881–93. (December 2012). doi:10.1007/s00438-012-0724-6. PMC 3881598. PMID 23080263.
- ^ “Three-dimensional structure of a type III glutamine synthetase by single-particle reconstruction”. J. Mol. Biol. 361 (4): 796–810. (August 2006). doi:10.1016/j.jmb.2006.06.026. PMID 16879836.
- ^ a b c d e f Garrett, Grisham (2017). Biochemistry (6th Edition). United States of America: Cengage Learning. pp. 886–889. ISBN 978-1-305-57720-6
- ^ “Evidence of covalent modification of glutamine synthetase in the purple sulfur bacterium”. FEMS Microbiology Letters 122 (1–2): 115–119. (1994). doi:10.1111/j.1574-6968.1994.tb07153.x.
- ^ “Purification and characterization of glutamine synthetase from Clostridium pasteurianum”. Biochemistry 25 (7): 1589–99. (Apr 1986). doi:10.1021/bi00355a021. PMID 2871863.
- ^ Bolay, Paul; Muro-Pastor, M.; Florencio, Francisco; Klähn, Stephan (27 October 2018). “The Distinctive Regulation of Cyanobacterial Glutamine Synthetase”. Life 8 (4): 52. doi:10.3390/life8040052.
- ^ “Nitrogen control in bacteria”. Microbiological Reviews 59 (4): 604–22. (December 1995). PMID 8531888.
- ^ a b “A cloned cyanobacterial gene for glutamine synthetase functions in Escherichia coli, but the enzyme is not adenylylated”. Proceedings of the National Academy of Sciences of the United States of America 78 (6): 3393–7. (June 1981). PMID 6115380.
- ^ “NtcA, a global nitrogen regulator from the cyanobacterium Synechococcus that belongs to the Crp family of bacterial regulators”. Molecular Microbiology 6 (13): 1853–9. (July 1992). PMID 1630321.
- ^ “Transcription of glutamine synthetase genes (glnA and glnN) from the cyanobacterium Synechocystis sp. strain PCC 6803 is differently regulated in response to nitrogen availability”. Journal of Bacteriology 179 (8): 2678–89. (April 1997). PMID 9098067.
- ^ “Glutamine synthetase inactivation by protein-protein interaction”. Proceedings of the National Academy of Sciences of the United States of America 96 (13): 7161–6. (June 1999). PMID 10377385.
- ^ “NtcA represses transcription of gifA and gifB, genes that encode inhibitors of glutamine synthetase type I from Synechocystis sp. PCC 6803”. Molecular Microbiology 35 (5): 1192–201. (March 2000). PMID 10712699.
- ^ “The sRNA NsiR4 is involved in nitrogen assimilation control in cyanobacteria by targeting glutamine synthetase inactivating factor IF7”. Proceedings of the National Academy of Sciences of the United States of America 112 (45): E6243-52. (November 2015). doi:10.1073/pnas.1508412112. PMID 26494284.
- ^ “A glutamine riboswitch is a key element for the regulation of glutamine synthetase in cyanobacteria”. Nucleic Acids Research. (August 2018). doi:10.1093/nar/gky709. PMID 30085248.
