密着結合

密着結合(みっちゃくけつごう)あるいはタイトジャンクション(英: tight junction)とは、隣り合う上皮細胞をつなぎ、さまざまな分子が細胞間を通過するのを防ぐ、細胞間結合のひとつ。
膜タンパク質及び膜脂質の移動を制限することにより、頂端領域と基底領域の領域を区分し、細胞の極性を維持すると考えられている。オリゴデンドロサイトのミエリン鞘にも同様の構造が存在する。
膜タンパク質としてオクルディン、トリセルリン、クローディンファミリー、JAMファミリー、アンギュリンファミリーがタイトジャンクションに局在し、ストランド(接着構造)形成はクローディンが担っている。 また、裏打ちタンパク質のZO-1などのZOファミリー、シングリンファミリーなどが密着結合の細胞質側に局在し、アクチン細胞骨格との相互作用に関与していると考えられている。
タイトジャンクションの形態学[編集]
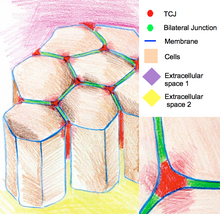
1963年にFarquharとPaladeはラット、モルモットの腺および管腔組織の様々な上皮細胞に形態の異なる3種類の細胞間接着分子を報告した[1]。これがタイトジャンクション、アドヘレンスジャンクション、デスモソームである。この論文では透過型電子顕微鏡観察である超薄切片像で隣り合う上皮細胞の形質膜が隙間なく完全に密着した形態学的な特徴と透過性バリアとしての機能を合わせて示している。1960年代後半には別の電子顕微鏡法である凍結割断レプリカ法によって、タイトジャンクションの膜密着部分では細胞内で粒子が紐状に並んだストランド構造がネットワークを形成し、ベルトとして細胞周囲を取り巻いていることが明らかになった[2]。
この構造はより正確にはバイセルラータイトジャンクション(bicellular tight junction、bTJ)とよばれる。3つの上皮細胞が接触するトリセルラーコンタクト(tricellular contact、TC)ではタイトジャンクションはバイセルラータイトジャンクションと異なる構造をしていると考えられており、トリセルラータイトジャンクション(tricellualr tight junction、tTJ)と呼ばれる。トリセルラータイトジャンクションに関しては1960年代から1970年代に複数の著者から凍結割断レプリカ法による電子顕微鏡観察が報告されている[2][3][4][5][6]。
中でもStaehelinらの報告はよく引用されている[2][3]。まずバイセルラータイトジャンクションのベルトはトリセルラーコンタクトに近づくと基底部側に折れ曲がり、お互いにほぼ寄り添ったまま基底部側に長く伸びる。そしてこの中心のベルトに向かって何本ものベルトが合流する。トリセルラーコンタクトの中心部はcentral sealing elementsとよばれる3対のTJストランドがあり、これらによって中心管(central tube)が構成される。central sealing elementsを構成するタイトジャンクションはバイセルラータイトジャンクションを構成する蛋白質とは異なると予想されていた。中心管の直径はおよそ12nmと言われており、高分子の傍細胞経路を制御すると考えられている[7][8][9]。ミオグロビンの有効分子径は1.9nm、アルブミンは3.6nm、γグロブリンは5.6nmであるため中心管を制御することで高分子医薬品を透過させることが可能となる。
タイトジャンクションの構成成分[編集]
クローディン[編集]
歴史[編集]
タイトジャンクションの構成分子に関しては長らく不明な時期が続いた。タイトジャンクションの構成成分の同定に関しては多くの日本人研究者が貢献しており、その歴史的な経緯は「小さな小さなクローディン発見物語」で記載されている[10]。1970年代にはタイトジャンクションを高純度に単離する方法がなかったため構成分子をモノクローナル抗体のスクリーニングによって同定された。この方法ではタイトジャンクションを多く含む膜分画を調製し、抗原として免疫し、その結果様々な抗原に対してできたモノクローナル抗体の中から免疫染色によってタイトジャンクションを標識するものだけを選び、その抗体を使ってタイトジャンクションに局在する抗原を同定し、クローニングする。この手法により1986年にStevensonらによって最初に同定されたタイトジャンクション構成分子がZO-1である[11]。ZO-1はタイトジャンクションの細胞質側を裏打ちする蛋白質で様々な分子と相互作用をすることが知られている。またZO-1はタイトジャンクションへの濃縮が極めてよいことから細胞間接着形成のすぐれたマーカーとしても知られている。1993年に古瀬幹夫、月田承一郎らはオクルディンというタイトジャンクションの膜タンパク質を発見した[12]。岡崎国立共同研究機構生理学研究所の月田承一郎研究室では当時はタイトジャンクションに隣接して存在する細胞間接着装置アドヘレンスジャンクション(カドヘリンが機能することで当時から知られていた)を齧歯類の肝臓から単離してその分子構築の解明を進めていた。彼らは研究の過程でアドヘレンスジャンクションと同じ分画にZO-1などタイトジャンクションに含まれる蛋白質が濃縮されていることに気がついた[13][14]。そこでこの細胞接着装置膜分画を従来の齧歯類ではなくヒヨコの肝臓から単離し、裏打ち蛋白質をできるだけ抽出した残りの膜をラットに免疫して作成したモノクローナル抗体を用いて細胞接着装置を同定しようとした。この時、膜タンパク質を同定するために少量のSDS(界面活性剤)を混ぜた抗原で免疫した。この方法で同定し、クローニングしたのがオクルディンであった。しかしその後、ES細胞から作成したオクルディン遺伝子欠失上皮細胞が発達したタイトジャンクションを形成し、オクルディンはタイトジャンクション形成に必須ではないことが示された[15]。そこで彼らは、ヒヨコ肝臓から得た細胞接着装置膜分画に戻り、この膜分画をさらに機械的に破砕して密度による分画などによりタイトジャンクションの精製を試みた。タイトジャンクションの単離には成功しなかったものの、この過程でタイトジャンクションマーカーであるオクルディンと一緒に振る舞う蛋白質バンドを一本見出し、そのアミノ酸配列決定から相同な2種類の蛋白質を同定した。これがタイトジャンクションの接着分子であるクローディンファミリーで最初に同定されたクローディン1とクローディン2である[16]。クローディン1またはクローディン2を持たないマウスL線維芽細胞に強制発現させると、いずれの場合も、もともと細胞接着活性を示さないL細胞が互いに強固に接着するようになった。さらに細胞間に巨大なタイトジャンクションストランドネットワークが形成された。オクルディンをL細胞に発現させてもこのようなネットワークは形成されないが、クローディンと同時に導入するとクローディンによって形成されたストランドにオクルディンが組み込まれた。
構造と機能[編集]
クローディンは4つの膜貫通ドメインと2つの細胞外ループをもつ分子量23kDの小さな4回膜貫通蛋白質である。W-GLW-C-Cというクローディンモチーフをもつ。ヒトやマウスでは少なくとも24種類のサブタイプの多遺伝子ファミリーを構成する。細胞生物学的な研究からクローディンの基本的な性質は以下のようにまとめられる[17]。
- 隣り合う細胞の両側から細胞接着部位に集積し、タイトジャンクションの細胞膜密着構造と膜内のストランド構造を形成する。
- 様々な組織で細胞あたり複数のサブタイプが上皮細胞に共発現していることが多く、上皮のタイプによって発現するサブタイプの組み合わせが異なる。
- 複数のクローディンが共発現している場合、一般にタイトジャンクションはこれらのクローディンがモザイク状に集まって形成される。
- タイトジャンクションを形成するクローディンのサブタイプには機能的な差異があり、細胞間隙の透過バリア形成に徹するバリア型クローディンとナトリウムイオンなど無機イオンや水などのような小分子を通す穴を形成するチャネル型クローディンが存在する。
代謝[編集]
クローディンは細胞内で合成された後、直接密着結合に輸送されるのではなく、一度細胞表面に輸送された後で密着結合に向かって移動し、クローディン同士の相互作用を介して密着結合に取り込まれる[18]。培養細胞におけるクローディン5の半減期は90分と非常に短い[19]。クローディン4の半減期は6時間でクローディン2の半減期は9時間である[20]。クローディンの密着結合への局在に脂質修飾であるパルミトイル化が重要という意見もある[21]。
立体構造[編集]
1998年に月田承一郎、古瀬幹夫らがクローディンを発見して以来、その立体構造は不明であった。一次構造から模式図が作成されていたのみであった。2014年に大阪大学と名古屋大学と東京大学の共同研究グループが世界ではじめてクローディンの立体構造を報告した[22][23]。彼らはSf9 insect cellという昆虫培養細胞発現系を用いてクローディンの発現と精製を試みた。異なるサブタイプをいくつも試し、マウスのクローディン15が発現量も多く、純度もよく精製することができた。良質な結晶作成のためクローディン機能として最も重要なTJストランド形成に最低限必要な領域のみ残したC末端欠損コンストラクトを作成し、脂質キュービック相法[24]を用いて結晶を作成した。兵庫県の大型放射光施設SPring-8でビームラインBL32XUを用いてX線回折データから2.4オングストローム分解能でクローディン15の結晶構造が得られた。この結果により、クローディンは4回膜貫通型の新規の折りたたみ構造をとること、細胞外領域のβシート構造はクローディンに保存された基本構造であること、クローディンの重合にはECHとTM3-β5との間での保存された疎水的な相互作用が重要であること、クローディン単量体は細胞外に掌を向けたような構造をしていること、細胞外表面領域がTJストランド中のイオン透過経路を作ることが明らかになった。
- クローディンは4回膜貫通型の新規の折りたたみ構造をとる
マウスのクローディン15は幅約3nmの大きさの分子であり4回膜貫通型タンパク質である。一次構造ではN末端からTM1、ECS1、ECH、TM2、TM3、ECS2、TM4と配列している。結晶構造からマウスのクローディン15は左巻きの4本ヘリックスバンドルからなる膜貫通領域(TM1-TM4)と2つの細胞外ループ部分が形成するβシート構造領域があることが明らかになった。膜貫通領域(TM1-TM4)にはグリシンやアラニンなどの小さな側鎖を多く含み、ヘリックス同士が固く巻き付いた構造をとっていた。膜貫通領域(TM1-TM4)の変位で難聴や低マグネシウム血症などの遺伝子疾患が報告されており4本ヘリックスバンドル構造はクローディンの生理機能に重要と考えられた。
- 細胞外領域のβシート構造はクローディンに保存された基本構造である
細胞外βシート領域は5本のβストランド(β1-β5)からなり、細胞外第1ループ(ECS1)の一部がβ1-β4として細胞外第2ループ(ECS2)の一部がβ5として含まれており、ひと続きの逆平行βシート構造を形成していた。これまで、細胞外第1ループと細胞外第2ループはそれぞれ別個のループ構造をもつと考えられていたが、実際にはループ構造ではなく、連続した1つの構造ドメインとして合体しているのが明らかになった。このフォールディングに重要なのがECS1中に存在するW-LW-C-Cという共通モチーフ配列であり、これはすべてのクローディンで保存されている。モチーフ配列中の2つのシステイン残基(Cys52とCys62)は分子内でジスルフィド結合を形成しており、β3とβ4の2つのストランドをつなぐことでβシートを構造を安定化していると考えられる。また、他の保存されたW-LW配列(Trp29、Leu48、Trp49)はβシート領域の根元側から脂質膜界面に突き刺さるように並んで配置しており、ヘリックスバンドル上部の裂け目の間に埋まっていた。この状態はあたかも錨(W-LW側鎖)をおろして細胞膜上にβシート領域を固定しているように見えることから、モチーフ配列は疎水的アンカーとして細胞外領域の構造を安定化するのに寄与しているとわかった。
- クローディンの重合にはECHとTM3-β5との間での保存された疎水的な相互作用が重要である
マウスのクローディン15分子は脂質キュービック相結晶中において単量体が横一列に並んだ状態でパッキングしており、隣接する分子間での横方向の相互作用には脂質膜界面に存在する細胞外の特定領域が関与していた。また観察された相互作用部位におけるアミノ酸変異導入とTJストランドの電子顕微鏡観察から、タンデムに隣接するECH(TM2直前の細胞外ヘリックス)とTM3-β5との間での保存された残基同士の疎水的な相互作用がTJストランドの形成に重要であることが示された。したがって結晶中でみられるこの直線上の並びは実際の生体内でみられるTJストランド中のクローディン重合体構造の一部を再現していると考えられる。
- クローディン単量体は細胞外に掌を向けたような構造をしている
構造解析の結果、マウスのクローディン15単量体は細胞外第1ループ(ECS1)と細胞外第2ループ(ECS2)による形成される5つのβストランドによって細胞外に掌をむけたような構造をとっている。5つのβシート構造を掌の左手の5本の指に例えるとクローディンは隣り合う細胞間であたかも掌同士が合わさるようにTJの細胞間バリアやチャネルを形成すると予想される。
- 細胞外表面領域がTJストランド中のイオン透過経路を作る
マウスのクローディン15はカチオン選択的なチャネル型TJを形成する。ECS1中の酸性残基(Asp55、Asp64)がその選択性に寄与している。これらの残基はβシート構造領域の端に偏って位置している。そのためマウスのクローディン15は細胞外表面領域が負に荷電される。他のクローディンサブタイプにおいても、この細胞外表面電荷がそれぞれのイオン選択性に応じた静電ポテンシャルをもっていることがホモロジーモデルから示された。TJストランド中においてクローディンの形成する掌状の荷電領域が傍細胞経路を覆うように配置することで透過・制限するイオンの選択性に寄与していることが示唆される。
クローディンファミリーに関して[編集]
ノックアウトマウスを用いたクローディンファミリーの解析[25]の結果から、バリア型クローディンとチャネル型クローディンが知られている。バリア型クローディンと考えられているのはクローディン1、クローディン4、クローディン5、クローディン7、クローディン11、クローディン14、クローディン18、クローディン19である。チャネル型クローディンは発現することで上皮細胞間にチャネルを形成して透過性を与える、あるいはタイトジャンクションストランド、のダイナミクスで透過性を与える。チャネル型クローディンにはクローディン2、クローディン10a、クローディン10b、クローディン15、クローディン16が知られている。またチャネル型クローディン以外の傍細胞経路としてリーク経路が知られている。比較的大きな分子量をもつ水溶性分子が水溶性分子が極めてわずかずつタイトジャンクションを通って漏れておりその経路をリーク経路という[26]。正常状態でリーク経路におけるわずかな漏れを説明するメカニズムの一つとしてタイトジャンクションのストランド構造が膜内の蛋白質ポリマーとしての切断と再結合を繰り返す動的な振る舞いが考えられる。
バリア型クローディン[編集]
血液脳関門は脳を守るバリアであり脳実質を囲む毛細血管内皮細胞のタイトジャンクションが重要な役割を担う。脳血管内皮細胞にはクローディン5の発現が特に多い。クローディン5以外にはクローディン12などの発現がみられる。クローディン5のノックアウトマウス(ホモ接合体)は生後1日以内で致死となる[27]。電子顕微鏡で形態評価を行うとクローディン5のノックアウトマウスにもタイトジャンクションストランド形成が確認され、脳血管のネットワークや組織構築は維持された。しかし小分子のトレーサーの通過は正常型マウスと大きく異なった。正常マウスは分子量443D、742D、1900Dのいずれも通過しなかった。しかしクローディン5ノックアウトマウスでは分子量443D、742Dのトレーサーは通過した。クローディン5のノックアウトマウス(ホモ接合体)の血液脳関門は分子量およそ800Dまでは通過するがそれより大きな分子は透過しない分子篩のような作用をしていると考えられた。クローディン5のノックアウトを行うと小分子の透過性のみ亢進するため、クローディン5の制御によって小分子の薬物輸送や水の透過性制御による脳浮腫の治療などが行える可能性がある。
Cambellらはマウスにクローディン5を標的とするsiRNAを全身投与し一時的にin vivoでクローディン5の発現を抑制してBBBの透過性を上げることに成功している[28]。このノックダウン効果は1週間未満で終息する。クローディン5とオクルディンを標的とするsiRNAをマウスに共投与し、脳微小血管内皮細胞で両者をノックダウンすると約3~5kDa程度の分子が血液脳関門を通過する報告がある[29]。一方、脳微小血管内皮にクローディン5を薬剤誘導性にノックダウンできるマウスを作成し、成熟マウスでクローディン5の持続的なノックダウンを行った場合、2~6週間以内にマウスが統合失調症様の症状を示し死亡する[30]。恒常的に1kDa以下の低分子が脳内に流入し続けると脳内環境が破綻し致命的な脳内炎症が生じることが示唆される[31]。またクローディン5の変異は統合失調症と関連している[32][33][34]。
- クローディン7と大腸炎
クローディン7の腸管上皮細胞特異的ノックアウトマウスは大腸炎のモデルマウスである。
- クローディン18と胃炎
クローディン18はプロトンバリアを構成すると考えられている。クローディン18のノックアウトマウス(ホモ接合体)は胃の壁細胞が成熟し胃酸分泌をはじめる生後4日目から胃炎の症状がみられる。同時に壁細胞やその分化した主細胞の減少がみられる[35]。
チャネル型クローディン[編集]
腸管上皮細胞シートは細胞間の選択的イオン透過性の高い臓器として知られている。腸管に発現が多い2つの細胞間チャネル型クローディンであるクローディン2とクローディン15のダブルノックアウトマウスはナトリウムイオンの上皮細胞間透過性が野生型マウスのおよそ20%にまで低下する。また離乳前後に三大栄養素の吸収不全で致死的になる[36]。クローディン12も腸管吸収上皮細胞に発現しているという報告があったが、用いられた抗体の特異性に問題があり[37]結果が再現できていない。また、クローディン2やクローディン15と異なり、クローディン12のノックアウトマウスの腸には表現型は報告されていない。チャネルとして機能するとする証拠もない。
オクルディン[編集]
最初に発見されたタイトジャンクションを構成する膜貫通蛋白質である[38]。ノックアウトマウスでもタイトジャンクションが形成されるため、タイトジャンクションにおける正確な役割は不明な点が多い[39][40]。クローディンファミリーと相互作用することでクローディンファミリー単独で形成するタイトジャンクションストランドよりも複雑なタイトジャンクションストランドを形成するという研究内容もある[41]。オクルディンノックアウトマウスはタイトジャンクションを構成でき、生存可能である。しかし成長遅延となり胃の壁壁細胞は消失する。また緻密骨の薄化、脳内石灰化、精巣萎縮、唾液腺の線条導管細胞質顆粒の消失、コルチ器の有毛細胞のアポトーシスが認められる。オクルディンノックアウトマウスがしめす脳内血管内皮細胞周辺のカルシウムの沈着は金属イオンの透過亢進が血液脳関門で生じていると考えられている[39]。コルチ器の有毛細胞のアポトーシスはクローディン14欠損によるDFNB29やトリセルリン変異によるDFNB49、アンギュリン2変異によるDFNB42に類似する[42]。コルチ器の有毛細胞のアポトーシスはオクルディンの欠損のためトリセルリンがバイセルラータイトジャンクションに導入された結果である。
分子量は65kDで短いN末端細胞質尾部、2つの細胞外ループおよび長いC末端細胞細胞質尾部をもつ4回膜貫通型蛋白質である[38][43][44][45][46][47]。オクルディンとトリセルリンとmarvelD3が相同性がありMARVELファミリー(またはTAMPファミリー)とよばれる[48][49]。C末端細胞質尾部にはZO-1やアクチンと相互作用をするのに必要なOCELドメインとよばれる構造がある[50]。オクルディンはbTJのリーク経路におけるmacromoleculeの透過とカベオリンエンドサイトーシスに関与している[51]。培養細胞でオクルディンをノックダウンすると6.25nmほどの分子の透過性が著しく亢進した[51]。3.6nm、70kDの分子の透過性を亢進させた別の報告も存在する[52]。TNFは上皮細胞の透過性を更新させることが知られているが、その作用はオクルディンを介していると考えられている[53][54][55][56][7]。オクルディンをノックダウンするとTNFを投与してもmacromoleculeの透過性が亢進しない[57]。TNFによっておこるmacromoleculeの透過性の亢進はOCELドメインのアクチンやZO-1との相互作用が関与する[50][58][59][60]。オクルディンとトリセルリンのダブルノックアウト細胞の解析から、オクルディンとトリセルリンが、クローディンが作るストランドの分岐点を安定化し網目構造の複雑性を維持する役割を持つ事が示唆されている。[61]
大腸菌[62]、デングウイルス[63]、ノロウイルス[64]、ロタウイルス[65]、緑膿菌[66]は感染時にオクルディンの発現を抑制、病原生物の侵入を容易にする。オクルディンは多くの病原微生物のターゲットとなっている。クローディン1とともにC型肝炎ウイルスの受容体である。培養細胞でオクルディンをノックダウンするとバイセルラータイトジャンクション内のトリセルリンが増加する[67]。これはオクルディンがバイセルラータイトジャンクションからトリセルリンを排除していることを意味する。
トリセルリン[編集]
トリセルラータイトジャンクションで最初に発見された構成蛋白質である[68]。別名はmarvelD2である。発見当初マウストリセルリンは分子量が63.6kDで、短いN末端細胞質尾部、2つの細胞外ループおよび長いC末端細胞細胞質尾部をもつ4回膜貫通型蛋白質として同定された。オクルディンとトリセルリンとmarvelD3が相同性がありMARVELファミリー(またはTAMPファミリー)とよばれる。C末端細胞質尾部にはZO-1やアクチンと相互作用をするのに必要なOCELドメインが保存されている[69]。C末端はオクルディンとの相同性が32%もある[9]。その後トリセルリンは4つのアイソフォームがあることがわかった[70]。ヒトのトリセルリン遺伝子(TRIC)にはTRIC-a、TRIC-a1、TRIC-b、TRIC-cなどがあるが単にトリセルリンと言われた場合は多くの場合最長のTRIC-aを指すことが多い。7つのエクソンを含み、エクソン2に4つの膜膜貫通領域がコードされ、C末端にOCELドメインがコードされる。TRIC-a1はエクソン3を欠く。TRIC-bはC末端のOCELドメインを欠く。TRIC-Cは選択的スプライシングの結果、エクソン2の膜貫通領域が2つになっている。C末端細胞質ドメインに変異があるとDFNB49という難聴の原因となる。C末端細胞質ドメインはアンギュリンファミリーとの相互作用に関与する。このドメインがアンギュリンファミリーと相互作用することでトリセルリンはトリセルラーコンタクトに局在する。トリセルリンは上皮[67][71][69]や内皮[72][73]のトリセルラーコンタクトの他に樹状細胞[74]、ミクログリア[75]、シュワン細胞[76]でも発現している。
DFNB49難聴を引き起こす変異トリセルリンのノックインマウスでは有毛細胞の変性があり進行性難聴をしめす[77]。そしてトリセルラータイトジャンクションにトリセルリンが局在せず、トリセルラーコンタクトでbTJの構造が分離していた。予想外にトリセルリンのノックアウトマウスは有毛細胞の変性による進行性難聴を示す。腸管上皮や血管内皮の傍細胞経路はWTと同様であり、透過型電子顕微鏡ではバイセルラータイトジャンクションの構造は維持された。
マウス上皮由来培養細胞(マウスEph4)でTRIC-aをノックダウンするとTERの低下と4kDのデキストランの透過性が亢進した。250kDの透過性は変化しなかった。形態学的にはトリセルラーコンタクト周囲のbTJの構造が乱れた[68]。トリセルリンのノックダウンはバイセルラータイトジャンクションとトリセルラータイトジャンクションの両方に影響を与えてしまうため、KrugらはユニークなアプローチでtTJの特性を示した[78]。培養細胞(MDCKⅡ)にTRIC-aを過剰発現させるとTERは変化せずに4kb、10kb、20kbの透過性が低下した。Krugらはトリセルラータイトジャンクションにも小分子の経路と大分子の経路があるが、トリセルラータイトジャンクションは傍細胞伝導率の1%しか関与しないため、イオン透過性が変化しないと考察した。また過剰発現で透過性が低下することからトリセルリンが大分子透過に関与すると主張した。そして中心管を3kDの蛍光つきデキストランが通過することを視覚化した。
培養細胞でオクルディンをノックダウンするとバイセルラータイトジャンクション内のトリセルリンが増加する[67]。これはオクルディンがバイセルラータイトジャンクションからトリセルリンを排除していることを意味する。
オクルディン同様にトリセルリンも病原微生物のターゲットとなっている。赤痢菌[79]はトリセルラータイトジャンクションを介して隣接する上皮細胞内に侵入し、緑膿菌[66]は一過性にトリセルリンをダウンレギュレートする。
アンギュリン[編集]
2000年に発表されたFL-REX法[80](蛍光局在化レトロウイルス媒介発現クローニング)を用いてトリセルリン以外のtTJの構成成分としてLipolysis-stimulated lipoprotein receptor (LSR)が見つかった[81]。LSRは免疫グロブリン様ドメインをもつ膜蛋白質であり、もともと既知のLDL受容体以外でトリグリセリドが豊富なリポプロテインの取り込みに関わる受容体の候補として同定された[82]。ヒトLSRは581アミノ酸からなり、細胞外Igドメイン、膜貫通ドメイン、細胞内ドメインからなる[83]。10個のエクソンからなり選択的スプライシングによってα、α'、βの3つのサブタイプが存在する。αタイプが全長翻訳されたものであり細胞外C末端、膜貫通領域、細胞内N末端からなる。α‘とβはC末端のジロイシンモチーフ(細胞質への輸送シグナル)がなく、βは膜貫通領域がほとんど完全にない。ノックアウトマウスのホモ接合体は胎生致死[84]であり、ヘテロ接合体は食物摂取後に血漿トリアシルグリセリドおよびコレステロールのレベルが上昇する[85]。そのためリポ蛋白脂質のクリアランスに関与すると考えられていた。培養細胞でLSRをノックダウンするとTERは低下し、4kD、10kD、40kDの蛍光つきデキストランの透過性が亢進した[81]。LSRをノックダウンした培養細胞のオクルディンの免疫染色で形態学的変化が認められた。オクルディンは通常はTJマーカーとして用いられるが、LSRをノックダウンした培養細胞ではトリセルラーコンタクトのオクルディンの染色が不連続になっており、オクルディンの蓄積がおこっていると考えられている。トリセルリンをノックダウンした培養細胞ではLSRはトリセルラーコンタクトに局在したままであるが、LSRをノックダウンした培養細胞ではトリセルリンがトリセルラーコンタクトに局在せず細胞膜全体に散在し、この表現型はLSRを外来性に再発現させると回復する。以上からLSRがトリセルリンをトリセルラーコンタクトに動員すると考えられる。LSRの細胞質領域とトリセルリンのC末端細胞質領域が相互作用する結果トリセルラーコンタクトにLSRとトリセルリンが共局在する。
多くの上皮細胞でLSRは発現している。しかし部位によってはトリセルリンがトリセルラーコンタクトに局在しているがLSRが発現していない上皮があった。例えば結腸では陰窩下部ではLSRが発現しているが陰窩上部ではLSRが発現していないがトリセルリンは陰窩全体でトリセルラーコンタクトに局在していた。以上のことからLSRに相同な遺伝子があることが予想された。マウスではLSRに相同な遺伝子としてILDR1[86]とILDR2[87][88]が知られていた。LSRを含めた3つの遺伝子全ての複数のスプライシングアイソフォームが存在する。いずれも一回膜貫通型蛋白質で細胞外Igドメイン、膜貫通ドメイン、細胞内ドメインからなっていた。3つの蛋白質は30%のアミノ酸同一性を共有していた。ILDR1は結腸陰窩上部、膀胱、唾液腺、嗅上皮、腎臓を含む広範な上皮組織、内耳コルチ器で認められた。ILDR2は網膜色素上皮細胞や神経周膜や脈絡叢などの神経組織を覆う上皮細胞で発現している。LSRをアンギュリン1、ILDR1をアンギュリン2、ILDR2をアンギュリン3と呼び、この3つの蛋白質をアンギュリンファミリーと呼ぶことが提唱されている[89]。アンギュリン1、アンギュリン2、アンギュリン3のいずれもトリセルラーコンタクトに局在していた。確認された範囲では全ての上皮で何らかのアンギュリンファミリーの蛋白質とトリセルリンが発現していた。一部の組織では複数のアンギュリンファミリーの蛋白質が確認された。アンギュリン1と同様にアンギュリン2、アンギュリン3も細胞質領域とトリセルリンのC末端細胞質領域が相互作用し、トリセルリンをトリセルラーコンタクトに動員した。アンギュリンファミリーの蛋白質がなぜ、トリセルラーコンタクトに局在するのかは不明である。また全てのアンギュリンファミリーのノックダウンはtTJだけではなくbTJにも影響をあたえ大分子と小分子の透過に影響を与えている。アンギュリン2の変異はDFNB42という進行性難聴の原因となる[90]。
上皮におけるトリセルリンやアンギュリンファミリーの研究は数多く報告されたが血管内皮のトリセルリンやアンギュリンファミリーに関しては長い間報告がなかった。2013年に岩本、古瀬らによってはじめて報告された[91]。非神経組織として小腸、膵臓、大血管、肺、結腸、肝臓、腎臓の血管内皮ではアンギュリンファミリーやトリセルリンは認められなかった。上皮組織では認められた。脳に関しては大脳や小脳を含む脳実質ではアンギュリン1とトリセルリンがトリセルラーコンタクトに局在していた。脈絡叢の血管内皮と脳室周囲器官(CVO)の血管内皮ではアンギュリン1とトリセルリンの発現は認められなかった。網膜内皮細胞にはアンギュリン1とトリセルリンがトリセルラーコンタクトに局在していた。また脳実質内の血管内皮ではアンギュリン2とアンギュリン3の発現は認められなかった。アンギュリン1は血管内皮では脳実質と網膜の血管内皮で特異的でありBBB成熟後に発現をしめす[92]。脳梗塞と多発性硬化症では血液脳関門のバリア機能が低下している[93]。多発性硬化症の動物モデルである実験的自己免疫性脳脊髄炎(EAE)のマウスの炎症部位ではアンギュリン1の発現が低下しており、また脳梗塞の動物モデルである中大脳動脈閉塞(MCAO)のマウスの血管閉塞側でもアンギュリン1の発現が低下していた[92]。
アンギュリン1のSer288がリン酸化するとトリセルラーコンタクトに局在し、リン酸化しない場合は脂質代謝に関わるという説がある[94]。またアンギュリン1の細胞質ドメインの脂質修飾であるパルミトイル化と細胞外ドメインの作用がアンギュリン1の三細胞接着部位への局在に重要という報告もある[95]。抗アンギュリン1抗体である#1~25は卵巣上皮癌の治療薬となる可能性がある[96]。
傍細胞経路[編集]
薬物を腸管上皮や血液脳関門を通過させるには経細胞経路または傍細胞経路を薬物が通過する必要がある[97]。上皮細胞または内皮細胞の細胞同士の隙間から物質輸送を行う経路を傍細胞経路という[98]。傍細胞経路には電荷選択性透過経路(charge-selective pathway)とサイズ選択性透過経路(size-selective pathwayまたはリーク経路、leak pathway)が知られている。バイセルラータイトジャンクションでは電荷選択性透過経路はチャネル型クローディン(Pore forming claudins)によって形成されると考えられている[99]。透過できるサイズや電荷は構成するクローディンによっても異なるが0.4nm未満の小分子が瞬時に通過できる(クローディン2では0.65 nm、クローディン15では0.8 nm)。電荷選択性透過経路のバリア機能はTERで評価される。クローディンのトランス相互作用でチャネルが形成される。しかしどのような構造変化でチャネルが開閉するかなどまだわからない点も多い。バイセルラータイトジャンクションではリーク経路は30~60nmまで透過可能と言われている。リーク経路の有力な仮説のひとつにdynamic strand modelというものがある[100]。dynamic strand modelではリーク経路はタイトジャンクション構成蛋白質と脂質の相互作用で形成されると考えられている(タイトジャンクション自体をprotein-lipid hybrid modelで考えている)。タイトジャンクション構成蛋白質の結合やタイトジャンクション構成蛋白質の膜状の移動の結果、高分子が傍細胞経路を通過する。オクルディンやトリセルリンが高分子のサイズを規定すると考えられている。高分子が一定の時間をかけて通過するのでトレーサーを用いて透過率を評価する。
電荷選択性透過経路はチャネル型クローディンがtrans相互作用の結果生じた孔を小分子が通過する。リーク経路はオクルディンがサイズを規定し逆ミセルの形態で高分子を通過させる[101]。オクルディンをノックダウンすることで6.25nmほどの高分子の透過性が亢進するのでオクルディンがバリアー機能を担っている。TNFによって高分子の透過性は亢進する[7]。またタイトジャンクションストランドへの傷害はリーク経路を亢進させる[102]。タイトジャンクションにはバイセルラータイトジャンクションの他、トリセルラータイトジャンクションが知られている。電荷選択性透過経路とリーク経路はそれぞれのタイトジャンクションに存在する。タイトジャンクション構成蛋白質の違いから両者の役割は異なると考えられている。トリセルラータイトジャンクションの特徴としては直径12 nmにおよぶ中心管の存在があげられる。形態学的な特徴から高分子が透過しやすいと予想された。トリセルラータイトジャンクションでは電荷選択性透過経路とリーク経路はいずれも中心管を通過するものと考えられている。トリセルリンの過剰発現で高分子の透過性が低下するがTERが低下しなかった。Krugらはこの現象をトリセルリンがリーク経路のサイズ制限を行っているためと考えた[78]。またトリセルラータイトジャンクションは傍細胞伝導率の1%しか関与しないためトリセルラータイトジャンクションのみの電荷選択性透過経路の透過率が変化してもTERは変化しないと考察した。
脚注[編集]
- ^ J Cell Biol. 1963 May 17:375-412. PMID 13944428
- ^ a b c Protoplasma. 1969;67(2):165-84. PMID 5346995
- ^ a b J Cell Sci. 1973 Nov;13(3):763-86. PMID 4203962
- ^ J Cell Biol. 1972 Jun;53(3):758-76. PMID 4337577
- ^ J Cell Biol. 1974 Jan;60(1):168-80. PMID 4203358
- ^ Acta Anat (Basel). 1985;122(1):35-8. PMID 4003026
- ^ a b c Semin Cell Dev Biol. 2014 Dec;36:166-76. PMID 25220018
- ^ Mol Biol Cell. 2009 Aug;20(16):3713-24. PMID 19535456
- ^ a b Eur J Cell Biol. 2011 Oct;90(10):787-96. PMID 21868126
- ^ 小さな小さなクローディン発見物語 ISBN 4897068509
- ^ J Cell Biol. 1986 Sep 103(3):755-66. PMID 3528172
- ^ J Cell Biol. 1993 Dec 123(6 Pt 2) 1777-88. PMID 8276896
- ^ J Cell Biol. 1991 Dec 115(5):1449-62. PMID 1955485
- ^ J Cell Biol. 1993 May 121(3):491-502. PMID 8486731
- ^ J Cell Biol. 1998 Apr 20 141(2) 397-408. PMID 9548718
- ^ J Cell Biol. 1998 Jun 29 141(7) 1539-50. PMID 9647647
- ^ Trends Cell Biol. 2006 Apr 16(4) 181-8. PMID 6537104
- ^ Mol Biol Cell. 2019 Jun 1;30(12):1406-1424. PMID 30943107
- ^ J Cell Biochem. 2012 Jul;113(7):2415-23. PMID 22389112
- ^ J Membr Biol. 2004 May 1;199(1):29-38. PMID 15366421
- ^ J Biochem. 2018 Apr 1;163(4):265-272. PMID 29186552
- ^ Science. 2014 Apr 18 344(6181) 304-7. PMID 24744376
- ^ 実験医学 Vol.32 No.14 2014 p2259-2262 ISBN 9784758101318
- ^ Proc Natl Acad Sci U S A. 1996 Dec 10;93(25):14532-5. PMID 8962086
- ^ Semin Cell Dev Biol. 2014 Dec 36 177-85. PMID 25305579
- ^ Annu Rev Physiol. 2011 73 283-309. PMID 20936941
- ^ J Cell Biol. 2003 May 12;161(3):653-60. PMID 12743111
- ^ J Gene Med. 2008 Aug;10(8):930-47, PMID 18509865
- ^ Sci Adv. 2015 Sep 4;1(8):e1500472. PMID 26491725
- ^ Mol Psychiatry. 2018 Nov;23(11):2156-2166. PMID 28993710
- ^ 橋本洋佑, 近藤昌夫, 竹田浩之, 「タイトジャンクションシール制御技術を利用した中枢神経疾患治療薬のためのDDS開発」『Drug Delivery System』 34巻 5号 2019年 p.374-384, doi:10.2745/dds.34.374, 日本DDS学会
- ^ J Hum Genet. 2006;51(12):1037-1045. PMID 16969581
- ^ Prostaglandins Leukot Essent Fatty Acids. 2005 Dec;73(6):441-5. PMID 16181776
- ^ Eur Psychiatry. 2004 Sep;19(6):354-7. PMID 15363474
- ^ Gastroenterology. 2012 Feb 142(2) 292-304. PMID 22079592
- ^ Gastroenterology. 2013 Feb;144(2):369-80. PMID 23089202
- ^ Fluids Barriers CNS. 2019 Sep;16(1):30. PMID 31511021
- ^ a b J Cell Biol. 1993 Dec;123(6 Pt 2):1777-88. PMID 8276896
- ^ a b Mol Biol Cell. 2000 Dec;11(12):4131-42. PMID 11102513
- ^ Biochim Biophys Acta. 2005 May 15;1669(1):34-42. PMID 15842997
- ^ J Cell Sci. 2013 Jan 15;126(Pt 2):554-64. PMID 23203797
- ^ Biol Open. 2014 Jul 25;3(8):759-66. PMID 25063198
- ^ Am J Physiol. 1997 Dec;273(6 Pt 1):C1859-67. PMID 9435490
- ^ J Cell Biol. 1997 Jan 27;136(2):399-409. PMID 9015310
- ^ J Cell Biol. 1996 Apr;133(1):43-7. PMID 8601611
- ^ Adv Drug Deliv Rev. 2005 Apr 25;57(6):883-917. PMID 15820558
- ^ Mol Cell Biol. 2012 Jan;32(2):242-50. PMID 22083955
- ^ Mol Biol Cell. 2010 Apr 1;21(7):1200-13. PMID 20164257
- ^ BMC Cell Biol. 2009 Dec 22;10:95. PMID 20028514
- ^ a b J Cell Biol. 1994 Dec;127(6 Pt 1):1617-26. PMID 7798316
- ^ a b Mol Biol Cell. 2013 Oct;24(19):3056-68. PMID 23924897
- ^ Am J Physiol Gastrointest Liver Physiol. 2011 Jun;300(6):G1054-64. PMID 21415414
- ^ J Clin Invest. 2005 Oct;115(10):2702-15. PMID 16184195
- ^ J Clin Invest. 2006 Oct;116(10):2682-94. PMID 17016558
- ^ J Cell Biol. 2010 Apr 5;189(1):111-26. PMID 20351069
- ^ Am J Pathol. 2005 Feb;166(2):409-19. PMID 15681825
- ^ J Cell Sci. 2010 Aug 15;123(Pt 16):2844-52. PMID 20663912
- ^ J Biol Chem. 1998 Nov 6;273(45):29745-53. PMID 9792688
- ^ J Mol Biol. 2005 Sep 9;352(1):151-64. PMID 16081103
- ^ J Biol Chem. 2000 Sep 22;275(38):29816-22. PMID 10887180
- ^ Mol Biol Cell 32 (8): 722–738. (2021 April). PMID 33566640.
- ^ Lab Invest. 2010 Aug;90(8):1152-68. PMID 20479715
- ^ J Gen Virol. 2004 Jul;85(Pt 7):1801-13. PMID 15218164
- ^ Gut. 2009 Aug;58(8):1070-7. PMID 19036950
- ^ J Cell Sci. 2004 Nov 1;117(Pt 23):5509-19. PMID 15494377
- ^ a b Respir Res. 2014 Feb 18;15:21. PMID 24548792
- ^ a b c Mol Biol Cell. 2008 Nov;19(11):4687-93. PMID 18768749
- ^ a b J Cell Biol. 2005 Dec 19;171(6):939-45. PMID 16365161
- ^ a b Am J Hum Genet. 2006 Dec;79(6):1040-51. PMID 17186462
- ^ Eur J Cell Biol. 2011 Oct;90(10):787-96. PMID 21868126
- ^ Med Mol Morphol. 2009 Dec;42(4):204-11. PMID 20033365
- ^ BMC Cell Biol. 2010 Sep 7;11:68. PMID 20822540
- ^ Cell Tissue Res. 2013 Mar;351(3):397-407. PMID 23250572
- ^ Biochem Biophys Res Commun. 2009 Nov 20;389(3):543-9. PMID 19748485
- ^ Biochem Biophys Res Commun. 2011 Jun 17;409(4):799-802. PMID 21624353
- ^ J Histochem Cytochem. 2010 Dec;58(12):1067-73. PMID 21097846
- ^ J Clin Invest. 2013 Sep;123(9):4036-49. PMID 23979167
- ^ a b Mol Biol Cell. 2009 Aug;20(16):3713-24. PMID 19535456
- ^ Cell Host Microbe. 2012 Apr 19;11(4):325-36. PMID 22520461
- ^ Proc Natl Acad Sci U S A. 2000 Mar 28;97(7):3062-6. PMID 10716735
- ^ a b J Cell Sci. 2011 Feb 15;124(Pt 4):548-55. PMID 21245199
- ^ J Biol Chem. 1999 May 7;274(19):13390-8. PMID 10224102
- ^ Structure and Function of the Lipolysis Stimulated Lipoprotein Receptor
- ^ Eur J Biochem. 2004 Aug;271(15):3103-14. PMID 15265030
- ^ J Biol Chem. 2008 Sep 12;283(37):25650-9. PMID 18644789
- ^ Biochem Biophys Res Commun. 2004 Oct 22;323(3):970-8. PMID 15381095
- ^ BMC Genomics. 2007 Feb 7;8:42. PMID 17286855
- ^ PLoS Genet. 2008 Jul 25;4(7):e1000137. PMID 18654634
- ^ J Cell Sci. 2013 Feb 15;126(Pt 4):966-77. PMID 23239027
- ^ Am J Hum Genet. 2011 Feb 11;88(2):127-37. PMID 21255762
- ^ Cell Struct Funct. 2014;39(1):1-8. PMID 24212375
- ^ a b J Cell Biol. 2015 Mar 16;208(6):703-11. PMID 25753034
- ^ Mol Biol Cell. 2017 Jul 15;28(15):2023-2034. PMID 28705832
- ^ Genes Cells. 2014 Jul;19(7):565-81. PMID 24889144
- ^ J Biol Chem. 2020 Mar 27;295(13):4289-4302. PMID 32079676
- ^ Cancer Res. 2018 Jan 15;78(2):516-527. PMID 29187404
- ^ Ther Deliv. 2014 Oct;5(10):1143-63. PMID 25418271
- ^ The Paracellular Channel. Biology, Physiology, and Disease. ISBN 9780128146354
- ^ Nat Rev Mol Cell Biol. 2016 Sep;17(9):564-80. PMID 27353478
- ^ Trends Cell Biol. 2010 Mar;20(3):142-9. PMID 20061152
- ^ Semin Cell Dev Biol. 2015 Jun;42:13-21. PMID 26003050
- ^ Ann N Y Acad Sci. 2012 Jun;1257:77-84. PMID 22671592
参考文献[編集]
- 小さな小さなクローディン発見物語 ISBN 4897068509
- 標準組織学総論 第5版 ISBN 9784260015318
- The Paracellular Channel. Biology, Physiology, and Disease. ISBN 9780128146354
- Molecular organization of tricellular tight junctions. Tissue Barriers. 2014 May 1;2:e28960. PMID 25097825
関連項目[編集]
外部リンク[編集]
- 脳科学辞典細胞接着分子
- タイトジャンクションのバリア機能を担う分子基盤(生化学 第78巻7号 p601-608(2006)より改変)
- 月田承一郎, 古瀬幹夫「タイトジャンクションを構成する4回膜貫通型タンパク質オクルディンとクローディンの発見 : Paracellular Pathway の新しい生理学へ向けて」『生化学』第72巻第3号、日本生化学会、2000年3月、155-162頁、ISSN 00371017、NAID 10006982711。
- 月田承一郎の2003年の講演会
- Multifunctional strands in tight junctions
- 古瀬幹夫、「トリセルラータイトジャンクションの分子構築」『YAKUGAKU ZASSHI』 2014年 134巻 5号 p.615-621, doi:10.1248/yakushi.14-00006-1, 日本薬学会
