核酸構造

核酸構造(かくさんこうぞう)では、DNAやRNAといった核酸の構造について記述する。化学的観点からは、DNAとRNAはきわめて類似している。核酸の構造はしばしば4つの階層(一次構造~四次構造)に分類される。
一次構造[編集]

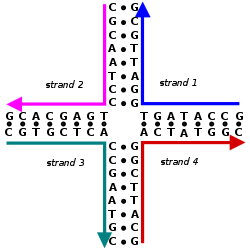
DNAまたはRNAの一次構造は直鎖状に並んだヌクレオチドの配列から構成される。各ヌクレオチドはホスホジエステル結合によって連結されている。ヌクレオチドは3つの要素からなる。
窒素塩基のアデニンとグアニンは構造的にはプリンであり、DNAでは9位の窒素とデオキシリボースの1'位の-OH基がグリコシド結合を形成する。シトシンとチミンはピリミジンで、1位の窒素とデオキシリボースの1'位の-OH基がグリコシド結合を形成する。RNAの場合、デオキシリボースの代わりにリボースが、チミンの代わりにウラシルが利用される。プリン塩基とピリミジン塩基の双方で、リン酸基の負に帯電した酸素とがデオキシリボースの5'位の-OH基がエステル結合を形成する[2]。あるヌクレオチドの5'位と他のヌクレオチドの3'位の炭素の間でホスホジエステル結合が形成されることで核酸の鎖が形成される[3]。核酸の一次構造(塩基配列)はDNAまたはRNA分子内でヌクレオチドが並ぶ順序を示しており、AGCT/Uの文字で表される。配列は5'末端から3'末端方向へ表され、分子の共有結合の構造が一意に表現される。アデニンとチミン(ウラシル)、グアニンとシトシンの構造は相補的であり、塩基対を形成する。ある配列に対し、逆向きに配置したときに各位置の塩基が相補的となる配列は、相補的配列と呼ばれる。DNAはセンス鎖とその相補的配列であるアンチセンス鎖からなる二本鎖である。
アルカリ金属イオンとの複合体[編集]
核酸の金属結合部位としては、リン酸、糖、塩基部分という3つの可能性がある。アルカリ金属イオンとの複合体の固体構造についての総説が執筆されている[5]。
二次構造[編集]
二次構造は塩基間の相互作用のセット、例えば鎖のどの部分が互いに結合しているかについての情報である。DNAの二重らせんでは、DNAの2本の鎖は水素結合によって互いに結合し、一方の鎖のヌクレオチドは他方のヌクレオチドと塩基対を形成する。DNA中の塩基はプリンとピリミジンに分類される。アデニンとグアニンはプリンであり、窒素を含む六員環と五員環からなる二重環構造から構成される。シトシンとチミンはピリミジンであり、窒素を含む六員環からなる単一の環構造である。プリン塩基は常にピリミジン塩基と対を形成する(グアニン(G)はシトシン(C)と、アデニン(A)はチミン(T)またはウラシル(U)と)。DNAの二次構造は、互いに巻き付いて二重らせん構造を形成する2本のポリヌクレオチド鎖で形成される塩基対のパターンを表現している。2本の鎖は塩基対間の水素結合によって整列するが、より強い力で2本の鎖が離れないようにしているのは塩基間のスタッキング相互作用である。これらのスタッキング相互作用はファンデルワールス力と疎水的相互作用によって安定化されており、局所的には多くの構造的差異が存在する[6]。二重らせん構造には2つの溝が存在し、大きさによって主溝(major groove)と副溝(minor groove)と呼ばれている。
RNAの二次構造には1本のポリヌクレオチドから構成されるものも含まれ、RNA分子中の相補性領域が折り畳まれることで塩基対形成が起こる。RNA分子には1本鎖の領域と2本鎖の領域の双方が存在していることが多い。RNAの二次構造の4つの基本要素はヘリックス、ループ、バルジ、ジャンクションである。ステムループ(ヘアピンループ)はRNAの二次構造で最もよく見られる要素である[7]。ステムループはRNA鎖が折り返されて塩基対を形成した構造であり、ステムと呼ばれる二重らせん部分とループと呼ばれる対合していない1本鎖領域が形成される[8]。RNAの二次構造はヘリックス、ループ、バルジといった二次構造要素についての実験的データに基づいて予測される。バルジとインターナルループは、二重らせん形成領域中に対合する相手のいないヌクレオチドが存在しているときに形成される。対合しないヌクレオチドが一方の鎖にのみ存在するときはバルジが、双方に存在するときはインターナルループが形成される。テトラループは4塩基からなるループ構造である。リボソームRNAでよく見られるテトラループには、UNCG、GNRA、CUUG(Nは4つの塩基、Rはプリン塩基のいずれか)という3つのファミリーが存在する。UNCGが最も安定なテトラループである[9]。シュードノットは、カブ黄斑モザイクウイルスで初めて同定されたRNAの二次構造である[10]。シュードノットはヘアピンループのループ領域のヌクレオチドがヘアピン外の1本鎖領域と対合してらせん構造を形成したものである。シュードノットの形状にはいくつかの種類が存在し、H型フォールドのシュードノットが最もよく研究されている。H型フォールドでは、ヘアピンループのヌクレオチドがヘアピンステム外の塩基と対合し2つ目のステムループ構造を形成する。その結果、2つのステムと2つのループを持つシュードノットが形成される[11]。シュードノットは多様な機能を持つ構造的要素で、ほとんどのクラスのRNAに見つかる。DotKnot-PW法がシュードノット構造の予測に利用される。DotKnot-PW法では、二次構造要素やH型シュードノットとの類似性のスコアリングに基づいて構造予測が行われる[12]。
三次構造[編集]


三次構造は三次元空間における原子の位置であり、幾何学的・立体的制約が考慮に入れられる。直鎖状のポリマーは大規模にフォールディングし、鎖の全長が特定の三次元的形状へと折り畳まれる。DNAが形成する二重らせんの三次構造には4つの点で差異が存在する。
- 右巻きか左巻きか
- ヘリックスのターンの長さ
- 1ターン当たりの塩基数
- 主溝と副溝の大きさの差[3]
DNA二重らせんの三次構造としては、B-DNA、A-DNA、Z-DNAの3種類が一般的に存在する。
B-DNAはin vivoで最も一般的なDNAの形状で、A-DNAよりも細く長いらせん構造である。その広い主溝はタンパク質がアクセスしやすくなっている。一方で、副溝は狭い。B-DNAは周囲の水分量が多い条件で好まれる構造であり、副溝の水和によってB-DNAが好まれるようである。B-DNAの塩基対はらせん軸とほぼ直交している。らせんがA型となるかB型となるかを決定する糖部分の立体配座(パッカリング、sugar pucker)はC2'-endo型である[13]。
A-DNAは、脱水条件で観察されるDNA二重らせんの形状で、B-DNAよりも短く幅広い。RNAの二重らせんはこれに類似した形状をとる。RNAとDNAからなる二重らせんは主にA型であるが、B型のRNA-DNA二重らせんも観察される[14]。RNA1本鎖中の2ヌクレオチドは、DNAとの対合がなくても局所的にB型構造をとることがある[15]。A-DNAは深く狭い主溝を持つため、タンパク質は容易にアクセスすることができない。一方、副溝は広く浅いためタンパク質がアクセス可能であるものの、副溝から得られる情報は主溝よりも少ない。A-DNAの塩基対はらせん軸に対して傾いており、らせん軸からも離れている。sugar puckerはC3'-endo型である。RNAの二重らせんでは2'-OH基がC2'-endo型立体配座をとるのを妨げているためA型構造となる[13]。長らくA-DNAは実験室で見られる人工物以上には見なされてこなかったが、現在ではいくつかの生物学的機能を持つことが示されている。
Z-DNAは比較的稀な左巻き二重らせんである。適切な配列と超らせんによる張力がかかった条件でin vivoでも形成されるが、その機能は不明である。A型やB型よりも細く長いらせん構造を持つ。Z-DNAの主溝は実際には溝を形成しておらず、狭い副溝を持つ。高塩条件下で最も好まれるコンフォメーションである。いくつかの塩基置換は存在するものの、プリンとピリミジンが交互に並んだ配列を必要とする。グアニンのN2-アミノ基は5'位のリン酸基と水素結合しており、これによってZ-DNAのプロトン交換速度が遅いこと、グアニン塩基が必要とされることが説明される。Z-DNAの塩基対はほぼらせん軸と直交している。Z-DNAでみられる反復構造の単位は1塩基対ではなくGpC配列の2塩基対であり、GpCとCpGではリン間の距離が異なる。GpC配列では塩基のスタッキングの大きな重なりがみられるが、CpG配列では重なりは小さい。Z-DNAの主鎖がジグザグしているのは、グアニンのグリコシド結合の立体配座をシトシンの立体配座が補償しているためである。グアニンの立体配座はsyn型、C2'-endo型で、シトシンではanti型、C3'-endo型である[13]。
直鎖状のDNA分子は回転する自由端が存在し、二重らせんの2本の鎖が互いに何回回転するかを変化させることで、細胞内でのさまざまな動的過程の変化を調節している。DNA分子の一部は環状で、そのため位相的な制約が存在する。近年、環状RNAも自然に広く存在し、多くの生物で発現していることが記載されている。共有結合によって閉じた環状DNA(cccDNAとしても知られる)の構造には位相的な制約が存在し、鎖が互いに対し何回回転しているかを変えることはできない。cccDNAは超らせん構造を形成していることもある。超らせんはリンキング数(linking number)によって特徴づけられる(詳細はDNA超らせんを参照)。細胞内のDNAは負の超らせんを形成して巻き戻りやすい傾向があり、超らせんを形成していないDNAよりも鎖の分離が容易である。超らせんDNAの構成要素にはソレノイド型とplectonemic型がある。plectonemic型の超らせんは原核生物で見られ、ソレノイド型の超らせんは主に真核生物で見られる。
四次構造[編集]
核酸の四次構造の概念は、タンパク質の四次構造と正確に同一であるわけではないものの類似している。四次構造は核酸の高次の組織化や、核酸と他の分子との相互作用を指す。核酸の高次の組織化として最も一般的にみられるものはクロマチンで、ヒストンとの相互作用によって高次構造が形成される。また、四次構造という語はリボソームやスプライソソームで見られる個々のRNA構造単位間でみられる相互作用を指して用いられることもある[16]。
出典[編集]
- ^ “Section 4.1: Structure of Nucleic Acids”. Molecular cell biology. New York: W.H. Freeman and CO. (2004). ISBN 978-0-7167-4366-8
- ^ “Structure of Nucleic Acids”. SparkNotes. 2019年8月26日閲覧。
- ^ a b Biochemistry (4th Edition). Englewood Cliffs, N.J: Prentice Hall. (2012). ISBN 978-0-13-800464-4
- ^ “The emergence of complexity: lessons from DNA”. PLoS Biology 2 (12): e431. (December 2004). doi:10.1371/journal.pbio.0020431. PMC 535573. PMID 15597116.
- ^ Katsuyuki, Aoki; Kazutaka, Murayama; Hu, Ning-Hai (2016). “Chapter 3, section3. Nucleic Acid Constituent complexes”. In Astrid, Sigel; Helmut, Sigel; Roland K.O., Sigel. The Alkali Metal Ions: Their Role in Life. Metal Ions in Life Sciences. 16. Springer. pp. 43–66. doi:10.1007/978-3-319-21756-7_3. ISBN 978-3-319-21755-0. PMID 26860299
- ^ “Geometric Patterns for Neighboring Bases Near the Stacked State in Nucleic Acid Strands”. Biochemistry 56 (10): 1426–1443. (2017). doi:10.1021/acs.biochem.6b01101. PMID 28187685.
- ^ “How RNA folds”. Journal of Molecular Biology 293 (2): 271–81. (October 1999). doi:10.1006/jmbi.1999.3001. PMID 10550208.
- ^ “RNA structure (Molecular Biology)”. 2019年8月31日閲覧。
- ^ “The effect of light on the quantity of phagosomes in the pigment epithelium”. Experimental Eye Research 23 (6): 623–35. (December 1976). doi:10.1016/0014-4835(76)90221-9. PMID 1087245.
- ^ “The tRNA-like structure at the 3' terminus of turnip yellow mosaic virus RNA. Differences and similarities with canonical tRNA”. Nucleic Acids Research 10 (6): 1929–46. (March 1982). doi:10.1093/nar/10.6.1929. PMC 320581. PMID 7079175.
- ^ “Pseudoknots: RNA structures with diverse functions”. PLoS Biology 3 (6): e213. (June 2005). doi:10.1371/journal.pbio.0030213. PMC 1149493. PMID 15941360.
- ^ “Predicting pseudoknotted structures across two RNA sequences”. Bioinformatics 28 (23): 3058–65. (December 2012). doi:10.1093/bioinformatics/bts575. PMC 3516145. PMID 23044552.
- ^ a b c “The anatomy of A-, B-, and Z-DNA”. Science 216 (4545): 475–85. (April 1982). doi:10.1126/science.7071593. PMID 7071593.
- ^ Chen X; Ramakrishnan B; Sundaralingam M (1995). “Crystal structures of B-form DNA-RNA chimers complexed with distamycin”. Nature Structural Biology 2 (9): 733–735. doi:10.1038/nsb0995-733.
- ^ “RNA approaches the B-form in stacked single strand dinucleotide contexts”. Biopolymers 105 (2): 65–82. (2016). doi:10.1002/bip.22750. PMID 26443416.
- ^ “Strucual Biochemistry/Nucleic Acid/DNA/DNA Structure”. 2012年12月11日閲覧。
