触媒三残基

触媒三残基(しょくばいさんざんき、英: Catalytic triad)とは、いくつかの酵素の活性部位に見られる3つの配位アミノ酸の一式である[1][2]。触媒三残基は、ヒドロラーゼおよびトランスフェラーゼ酵素(例えば、プロテアーゼ、アミダーゼ、エステラーゼ、アシルラーゼ、リパーゼ、およびβ-ラクタマーゼ)で最も一般的に見られる。酸-塩基-求核剤 三残基は、共有結合触媒のための求核性残基を生成するための一般的なモチーフである。この残基は電荷リレーネットワークを形成して求核剤を分極および活性化し、基質を攻撃して共有結合中間体を形成し、加水分解されて生成物を放出し、遊離酵素を再生する。求核剤は、最も一般的にはセリンやシステインアミノ酸であるが、時にはスレオニンまたはセレノシステインも含まれている。酵素の三次元構造は、配列上(一次構造)では離れていても、三残基が正確な方向にまとまっていることを示している[3]。
機能(および三残基の求核剤)の分岐進化と同様に、触媒三残基は収斂進化の最良の例のいくつかを示している。触媒作用に対する化学的制約により、同じ触媒解明が、少なくとも23の別々のスーパーファミリーで独立して展開している。その作用機序は、生化学的に最もよく研究されているものの一つである[4][5]。
歴史[編集]
トリプシンとキモトリプシンは、1930年代に初めて精製された酵素である[6]。1950年代には、トリプシンとキモトリプシンのそれぞれのセリンが触媒的求核剤として同定された(ジイソプロピルフルオロリン酸修飾)[7]。キモトリプシンの構造は、1960年代にX線結晶構造解析により解明され、活性部位に触媒三残基が配向していることが明らかになった[8]。他のプロテアーゼの配列が決定され、整理されて、現在はS1ファミリーと呼ばれる関連するプロテアーゼのファミリーが明らかにされた[9][10][11]。同時に、進化的に無関係なパパインおよびサブチリシンプロテアーゼの構造は類似の三残基を含んでいることが見いだされた。他の三残基メンバーによる求核剤の活性化のための「電荷リレー」メカニズムは、1960年代後半に提案された[12]。1970年代から80年代にかけて、X線結晶構造解析によってより多くのプロテアーゼの構造が解明され、(TEVプロテアーゼといった)相同な三残基および類似した(パパインといった)三残基が発見された[13][14][15]。1990年代から2000年代にかけて、プロテアーゼを構造的に関連した酵素スーパーファミリーに分類したMEROPS分類システムは、20以上のスーパーファミリーにおける三残基の収斂進化のデータベースとしての役割を果たしている[16][17]。進化に対する化学的制約が、どのようにして同じ三残基の幾何形状に非常に多くの酵素ファミリーの収斂のにつながったのかを理解することは2010年代に発展した[2]。
それらの最初の発見以来、酵素の正確な触媒機構について詳細な研究が増えた。1990年代と2000年代には、低障壁水素結合が触媒作用に寄与しているのか[18][19][20]、それとも通常の水素結合で機構を説明するのに十分なのか[21]、ということが特に議論された[22]。触媒三残基が使用する電荷リレー型共有結合触媒に関する膨大な研究の結果、生化学の中で最も特徴的な機構が解明された[4][5][21]。
機能[編集]
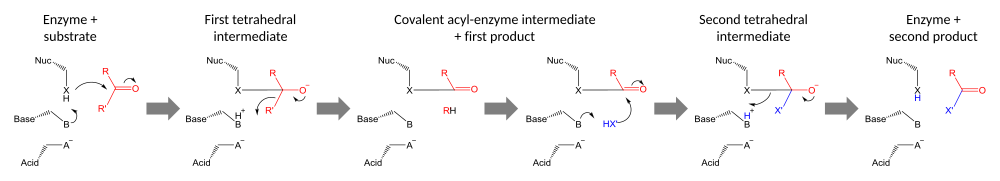
触媒三残基を含む酵素は、基質を分割する(加水分解酵素)か、基質の一部分を第二の基質に移す(転移酵素)かの2つの反応タイプのいずれかに三残基を使用する。三残基は、酵素の活性部位にある相互に依存する残基の集合であり、他の残基(例えば、結合部位やオキシアニオンホール)と協働して求核的触媒作用 (英語版) を達成するために作用する。これらの三残基が一緒に作用して求核剤メンバーの反応性を高め、基質との共有結合中間体を生成し、それが分解されて触媒反応が完了する。
機構[編集]
触媒三残基は、残基を求核剤として用いて共有結合触媒反応を行う。求核性残基の反応性は、他の三残基メンバーの官能基によって増加する。求核性残基は、それ自体が酸によって結合および安定化されている塩基により、分極および配向される。
触媒反応は2段階で行われる。まず、活性化された求核剤がカルボニル炭素を攻撃し、カルボニル酸素に電子を受け入れさせ、四面体中間体を形成する。この中間体への負電荷の蓄積は、通常、活性部位内のオキシアニオンホールによって安定化される。次に、中間体は崩壊してカルボニルに戻り、基質の前半を放出し、後半はアシル酵素中間体として酵素に共有結合したままになる。この最初の脱離基の放出は、多くの場合、塩基によるプロトンの供与によって促進される。
触媒反応の第二段階は、第二の基質の攻撃によるアシル酵素中間体の分解である。この基質が水であれば加水分解が行われ、有機分子であればその分子が第一の基質に移動する。この第二の基質による攻撃は、新しい四面体中間体を形成し、酵素の求核剤を放出し、第二の生成物を放出し、遊離酵素を再生することによって分解する[23]。
触媒三残基の例[編集]

例えばキモトリプシンの場合は、195番目のセリン側鎖が57番目のヒスチジンのイミダゾール環に近接し、さらにイミダゾール環の-NH基が102番のアスパラギン酸のカルボキシ基に近接している。
この節の加筆が望まれています。 |
脚注[編集]
- ^ Dodson G, Wlodawer A (1998). “Catalytic triads and their relatives”. Trends Biochem. Sci. 23 (9): 347–52. doi:10.1016/S0968-0004(98)01254-7. PMID 9787641.
- ^ a b Buller AR, Townsend CA (2013). “Intrinsic evolutionary constraints on protease structure, enzyme acylation, and the identity of the catalytic triad”. Proc. Natl. Acad. Sci. U.S.A. 110 (8): E653–61. Bibcode: 2013PNAS..110E.653B. doi:10.1073/pnas.1221050110. PMC 3581919. PMID 23382230.
- ^ Stryer L, Berg JM, Tymoczko JL (2002). “9 Catalytic Strategies”. Biochemistry (5th ed.). San Francisco: W.H. Freeman. ISBN 9780716749554
- ^ a b Perutz, Max (1992). Protein structure. New approaches to disease and therapy. New York: W.H. Freeman and Co. ISBN 9780716770213
- ^ a b Neurath H (1994). “Proteolytic enzymes past and present: the second golden era. Recollections, special section in honor of Max Perutz”. Protein Sci. 3 (10): 1734–9. doi:10.1002/pro.5560031013. PMC 2142620. PMID 7849591.
- ^ Ohman KP, Hoffman A, Keiser HR (1990). “Endothelin-induced vasoconstriction and release of atrial natriuretic peptides in the rat”. Acta Physiol. Scand. 138 (4): 549–56. doi:10.1111/j.1748-1716.1990.tb08883.x. PMID 2141214.
- ^ Dixon GH, Kauffman DL, Neurath H (1958). “Amino Acid Sequence in the Region of Diisopropyl Phosphoryl Binding in Dip-Trypsin”. J. Am. Chem. Soc. 80 (5): 1260–1. doi:10.1021/ja01538a059.
- ^ Matthews BW, Sigler PB, Henderson R, Blow DM (1967). “Three-dimensional structure of tosyl-α-chymotrypsin”. Nature 214 (5089): 652–656. Bibcode: 1967Natur.214..652M. doi:10.1038/214652a0. PMID 6049071.
- ^ Walsh KA, Neurath H (1964). “Trypsinogen and Chymotrypsinogen as Homologous Proteins”. Proc. Natl. Acad. Sci. U.S.A. 52 (4): 884–9. Bibcode: 1964PNAS...52..884W. doi:10.1073/pnas.52.4.884. PMC 300366. PMID 14224394.
- ^ de Haën C, Neurath H, Teller DC (1975). “The phylogeny of trypsin-related serine proteases and their zymogens. New methods for the investigation of distant evolutionary relationships”. J. Mol. Biol. 92 (2): 225–59. doi:10.1016/0022-2836(75)90225-9. PMID 1142424.
- ^ Lesk AM, Fordham WD (1996). “Conservation and variability in the structures of serine proteinases of the chymotrypsin family”. J. Mol. Biol. 258 (3): 501–37. doi:10.1006/jmbi.1996.0264. PMID 8642605.
- ^ Blow DM, Birktoft JJ, Hartley BS (1969). “Role of a buried acid group in the mechanism of action of chymotrypsin”. Nature 221 (5178): 337–40. Bibcode: 1969Natur.221..337B. doi:10.1038/221337a0. PMID 5764436.
- ^ Gorbalenya AE, Blinov VM, Donchenko AP (1986). “Poliovirus-encoded proteinase 3C: a possible evolutionary link between cellular serine and cysteine proteinase families”. FEBS Lett. 194 (2): 253–7. doi:10.1016/0014-5793(86)80095-3. PMID 3000829.
- ^ Bazan JF, Fletterick RJ (1988). “Viral cysteine proteases are homologous to the trypsin-like family of serine proteases: structural and functional implications”. Proc. Natl. Acad. Sci. U.S.A. 85 (21): 7872–6. Bibcode: 1988PNAS...85.7872B. doi:10.1073/pnas.85.21.7872. PMC 282299. PMID 3186696.
- ^ Phan J, Zdanov A, Evdokimov AG, Tropea JE, Peters HK, Kapust RB, Li M, Wlodawer A, Waugh DS (2002). “Structural basis for the substrate specificity of tobacco etch virus protease”. J. Biol. Chem. 277 (52): 50564–72. doi:10.1074/jbc.M207224200. PMID 12377789.
- ^ Rawlings ND, Barrett AJ (1993). “Evolutionary families of peptidases”. Biochem. J. 290 (1): 205–18. doi:10.1042/bj2900205. PMC 1132403. PMID 8439290.
- ^ Rawlings ND, Barrett AJ, Bateman A (2010). “MEROPS: the peptidase database”. Nucleic Acids Res. 38 (supl_1): D227–33. doi:10.1093/nar/gkp971. PMC 2808883. PMID 19892822.
- ^ Frey PA, Whitt SA, Tobin JB (1994). “A low-barrier hydrogen bond in the catalytic triad of serine proteases”. Science 264 (5167): 1927–30. Bibcode: 1994Sci...264.1927F. doi:10.1126/science.7661899. PMID 7661899.
- ^ Ash EL, Sudmeier JL, De Fabo EC, Bachovchin WW (1997). “A low-barrier hydrogen bond in the catalytic triad of serine proteases? Theory versus experiment”. Science 278 (5340): 1128–32. Bibcode: 1997Sci...278.1128A. doi:10.1126/science.278.5340.1128. PMID 9353195.
- ^ Agback P, Agback T (2018). “Direct evidence of a low barrier hydrogen bond in the catalytic triad of a Serine protease”. Sci. Rep. 8 (1): 10078. Bibcode: 2018NatSR...810078A. doi:10.1038/s41598-018-28441-7. PMC 6031666. PMID 29973622.
- ^ a b Warshel A, Papazyan A (1996). “Energy considerations show that low-barrier hydrogen bonds do not offer a catalytic advantage over ordinary hydrogen bonds”. Proc. Natl. Acad. Sci. U.S.A. 93 (24): 13665–70. Bibcode: 1996PNAS...9313665W. doi:10.1073/pnas.93.24.13665. PMC 19385. PMID 8942991.
- ^ Schutz CN, Warshel A (2004). “The low barrier hydrogen bond (LBHB) proposal revisited: the case of the Asp... His pair in serine proteases”. Proteins 55 (3): 711–23. doi:10.1002/prot.20096. PMID 15103633.
- ^ Shafee T (2014). Evolvability of a viral protease: experimental evolution of catalysis, robustness and specificity (PhD thesis). University of Cambridge. doi:10.17863/CAM.16528。
関連項目[編集]
外部リンク[編集]
この節の加筆が望まれています。 |