RBM10
RBM10(RNA-binding motif 10)はRBM10遺伝子にコードされたタンパク質[5][6][7][8]。ヒトの遺伝子はX染色体上のXp11.23に位置する。RBM10は選択的スプライシングを調節する因子である[9][10][11]。選択的スプライシングは転写後のpre-mRNAに作用して単一遺伝子から複数のタンパク質アイソフォームを生成する遺伝子発現の調節機構であり、細胞に機能的多様性と複雑性を作り出す[12]。RBM10は多数の遺伝子の発現に組み込まれ[9][10][13][14][15]、細胞増殖やアポトーシスなどさまざまな細胞過程に関与する[10][16]。RBM10遺伝子の変異は、出生前後に多くが致死となるX連鎖型先天異常のTARP症候群を引き起こし、成人でのさまざまながんなどの疾病に関わる[17][18][19][20][21][22]。
遺伝子とタンパク質
[編集]RBM10遺伝子の長さは約41.6 kb、24個のエクソンを含む。メスの細胞ではX染色体不活性化の制御を受け[6][7]、2つの遺伝子のうちの1つがヘテロクロマチン形成によりその発現(転写)が抑制(サイレンシング)される。
RBMタンパク質はRNA結合タンパク質の大きなファミリーを成し、ヒトでは52種類のRBMタンパク質が同定されている。それぞれはRNA認識モチーフ(RNA recognition motif: RRM)と呼ばれるRNA結合ドメインを1つまたは複数含む。RBM10は2つのRRM(RRM1とRRM2)を含み、さらに2つのジンクフィンガー(ZnF)、オクタマーリピート(OCRE)、3つの核局在化シグナル(NLS)、グリシンリッチドメイン(Gパッチ)などのドメインから成る。RBM10のアミノ酸配列は哺乳類間で保存され、ヒトとマウスの配列はアイソフォーム1で96%が同一であり[23]、RBM10の分子機能がヒトと齧歯類で本質的に同じであることが示唆される。
RBM10は一次転写産物に起こる選択的スプライシングにより複数のアイソフォームが作り出される。主要アイソフォームの1から4は、エクソン4のアミノ酸配列とエクソン10の最後のコドンのバリン残基の有無で異なる。アイソフォーム1(930残基)はエクソン4の配列とこのバリン残基を含む。アイソフォーム4(929残基)はこのバリンを含まない。アイソフォーム3(853残基)はエクソン4の配列を含まず、アイソフォーム2(852残基)はこのバリン残基をも含まない。アイソフォーム5(995残基)は、アイソフォーム1のN末端に65のアミノ酸残基が付加した形となる[24]。
機能
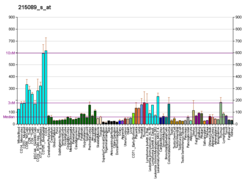
[編集]RBM10は、ほぼすべての細胞種に、そして増殖中と静止期の双方の細胞に発現が見られ、一般に、転写の活発な細胞でより強く発現する[25]。
選択的スプライシングの調節では、RBM10は標的pre-mRNAから成熟mRNAを生成する過程においてカセットエクソンまたは選択的エクソンと呼ばれる特定のエクソンのスキッピング(非取込み)反応に与る。また、低頻度ながら5'スプライス部位の選択やその他の選択的スプライシング反応に与ることがある[9][10][11][26]。エクソンスキッピングの過程では、RBM10はカセットエクソン両端の3'スプライス部位と5'スプライス部位に近接して結合し、これらスプライス部位のそれぞれの対合とスプライシング複合体による認識を妨げてカセットエクソンから離れたスプライス部位の対合を促進する。その結果、カセットエクソンは隣接する上流と下流のイントロンとともにmRNAには取り込まれずに切り出される、と示唆されている[9][10][26]。
RBM10が標的とするRNAの多様性は、RBM10が酸化的リン酸化などの代謝過程や、細胞増殖、アポトーシス、細胞接着、アクチン/細胞骨格の再構成などに関連したさまざまな経路、そしてがんや神経変性疾患など多様な疾患に関わることを示唆する[10][16][27]。こうしたデータやRBM10の普遍的発現は、RBM10は細胞の基本的構成要素でありさまざまな細胞過程に関わることを示している。選択的スプライシングの調節に加え、RBM10は他の反応にも関与する。例えば心臓の抗肥大調節因子pre-mRNAのポリアデニル化反応におけるSTARポリ(A)ポリメラーゼの共調節因子としての作用[28]、あるいはアンジオテンシンII受容体(ATR)mRNAの3' UTRへの結合によるATR mRNAの安定化[29]、let-7g miRNA前駆体への会合によるlet-7g miRNA生合成の調節[30]、p53の負の調節因子であるMDM2との結合によるp53の安定化[31]、細胞周期の停止[32][33]、そして抗ウイルス反応への関与などが示されている[34]。
RBM10は細胞核内で転写とスプライシングが起こる核質とS1-1 nuclear body(S1-1 NB)と呼ばれる膜を持たない核区画に局在する[25]。S1-1 NBは核当たり10個から40個程度、サイズは約0.5 µmであり、細胞種や細胞条件でこれらの数値は変わる。RNAポリメラーゼIIによる転写が低下すると、S1-1 NBは核質のRBM10を隔離して大きくなり、転写の回復でRBM10とS1-1 NBは元の状態に戻る[25]。S1-1 NBは核スペックルと部分的に重なりあうことが多く[25][35]、これら核区画化領域間にスプライシング反応における密接な機能的関係性のある事を示唆する。
調節
[編集]メスの細胞では、2本のX染色体の1つにおいてその大部分の遺伝子がヘテロクロマチン構造となり、転写は抑制された状態になる。RBM10遺伝子にもこのX染色体の不活性化が起こる[6][7][36]。加えて、RBM10にはその細胞内レベルを制御するその他の機構がいくつか存在する。選択的スプライシングによりRBM10はエクソン6または12を除去し、過剰発現時にpre-mRNAレベルを自己調節する。ここではこれらエクソンの除去(スキッピング)に伴い、翻訳終止コドンが転写体内部に導入され、生じた転写産物はNMD(nonsense-mediated mRNA decay)の機構で分解・処理される[14]。また、RNAポリメラーゼIIの転写減少時にはRBM10はS1-1 NBへ隔離される[25]。さらに、RBM10は翻訳後修飾を受ける。さまざまな刺激や細胞環境の変化に応答して多くの部位がリン酸化される(UniProtKB-P98175; PhosphoSitePlus RBM10)。またユビキチン化[37][38]や、アセチル化[39]、そしてメチル化[40]も起こる。
臨床的意義
[編集]RBM10の変異はヒトのさまざまな疾患に関連する。RBM10の変異が引き起こす表現型は発生段階や組織によって異なる。その典型的な例は多様な発生奇形を特徴とする新生児のTARP症候群[17][18]や成人の肺腺がん[19]や膀胱がん[20]などのさまざまながんに見られる。これらの疾患は女性よりも男性に一般的である[41][42][43]。細胞内のRBM10遺伝子のコピー数の違い(男性は1つ、女性は2つ)がその理由の1つと考えられる。RBM10の変異は分子全体にわたって生じ、疾病に関わるそれらの多くは分子機能が欠落あるいは減少するヌル変異であることが多い。TARP症候群は一般的に出生前後に致死となるが[17][44][45]、11歳、14歳、28歳の患者も報告されている[9][46][47]。RBM10の変異は腎臓がん[48][49][50]、膵臓がん[51][52]、大腸がん[53][54]、甲状腺がん[55][56][57]、乳がん[58]、胆管がん[59][60]、前立腺がん[58]、そして髄膜腫やアストロブラストーマの脳腫瘍[61][62]などのがんでも同定されている[63]。
NUMBは、最もよく研究されたRBM10の下流エフェクターである。RBM10はNUMB転写産物のエクソン9のスキッピングを促進し、生じたNUMBアイソフォームはNotch受容体のユビキチン化とこれに続くプロテアソームによる分解を誘導してNotchシグナリング(細胞増殖経路)を阻害する[10][21][64]。さまざまながんにおいて、RBM10の選択的スプライシング調節活性が不活性化したり低下する変異では、NUMBはエクソン9の配列の残ったアイソフォームとなり、その結果Notch経路は阻害されずにがん細胞の増殖が促進する[10][65][66]。
RBM10は細胞増殖を抑制し[10][29][31][65][66][67][68]、アポトーシスを促進する[29][31][66][67][69][70]。したがって、RBM10は一般的にがん抑制因子と考えられる。しかしながら、細胞の構成要素や細胞経路の活性の異なる細胞環境下に、RBM10は発がんプロモーターまたは増殖促進因子として作用する可能性がある[16][23][71]。この典型例は膵管腺がん(PDAC)患者に見られる。このがんの一般的な5年生存率は7–8%未満であるが、RBM10に変異を有する患者では、顕著に高い生存率が示されている[51][72][73]。
パラログとスプライシングネットワーク
[編集]RBM5とRBM6はRBM10のパラログ(ゲノム進化の過程で遺伝子重複によって生じた遺伝子群)である。これらは一般的にがん抑制因子として機能し[10][74][75][76][77][78][79][80]、変異は肺がんにしばしば同定される[22]。RBM5、RBM6、RBM10はいずれも選択的スプライシングを調節し[10][81][82]、一般的に異なるRNAに作用する。しかしながら特定のケースでは、同じRNAに作用し、相乗的または拮抗的な作用をつくり出す[10]。RBM5とRBM10には交差調節(crossーregulation)が働き、RBM10は選択的スプライシングとこれに共役したNMDによってRBM5転写体のレベルを減少させる[14]。さらに、RBM10レベルの変動(ノックダウンや過剰発現)は、RBM5を含む複数のスプライシング調節因子に起こるスプライシングに変化を引き起こし、またRBM10自身を含む他のスプライシング調節因子の発現にも大きく影響する[9][14]。さらにRBM10の一次転写体は、未同定のスプライシング調節因子によるいくつかの選択的スプライシングを受け、複数のアイソフォームを作り出す。これらのデータは、RBM5、RBM6、RBM10、そしてその他のスプライシング調節因子の間に選択的スプライシング反応のネットワークが作動することを示している[83]。
出典
[編集]- ^ a b c GRCh38: Ensembl release 89: ENSG00000182872 - Ensembl, May 2017
- ^ a b c GRCm38: Ensembl release 89: ENSMUSG00000031060 - Ensembl, May 2017
- ^ Human PubMed Reference:
- ^ Mouse PubMed Reference:
- ^ Nagase, T.; Seki, N.; Tanaka, A.; Ishikawa, K.; Nomura, N. (1995-08-31). “Prediction of the coding sequences of unidentified human genes. IV. The coding sequences of 40 new genes (KIAA0121-KIAA0160) deduced by analysis of cDNA clones from human cell line KG-1”. DNA research: an international journal for rapid publication of reports on genes and genomes 2 (4): 167–174, 199–210. doi:10.1093/dnares/2.4.167. ISSN 1340-2838. PMID 8590280.
- ^ a b c Coleman, M. P.; Ambrose, H. J.; Carrel, L.; Németh, A. H.; Willard, H. F.; Davies, K. E. (1996-01-01). “A novel gene, DXS8237E, lies within 20 kb upstream of UBE1 in Xp11.23 and has a different X inactivation status”. Genomics 31 (1): 135–138. doi:10.1006/geno.1996.0022. ISSN 0888-7543. PMID 8808293.
- ^ a b c Thiselton, Dawn L.; McDowall, Jennifer; Brandau, Oliver; Ramser, Juliane; d'Esposito, Fabiana; Bhattacharya, Shomi S.; Ross, Mark T.; Hardcastle, Alison J. et al. (2002-04). “An integrated, functionally annotated gene map of the DXS8026-ELK1 interval on human Xp11.3-Xp11.23: potential hotspot for neurogenetic disorders”. Genomics 79 (4): 560–572. doi:10.1006/geno.2002.6733. ISSN 0888-7543. PMID 11944989.
- ^ Inoue, A.; Takahashi, K. P.; Kimura, M.; Watanabe, T.; Morisawa, S. (1996-08-01). “Molecular cloning of a RNA binding protein, S1-1”. Nucleic Acids Research 24 (15): 2990–2997. doi:10.1093/nar/24.15.2990. ISSN 0305-1048. PMC 146028. PMID 8760884.
- ^ a b c d e f Wang, Yongbo; Gogol-Döring, Andreas; Hu, Hao; Fröhler, Sebastian; Ma, Yunxia; Jens, Marvin; Maaskola, Jonas; Murakawa, Yasuhiro et al. (2013-09). “Integrative analysis revealed the molecular mechanism underlying RBM10-mediated splicing regulation”. EMBO molecular medicine 5 (9): 1431–1442. doi:10.1002/emmm.201302663. ISSN 1757-4684. PMC 3799496. PMID 24000153.
- ^ a b c d e f g h i j k l Bechara, Elias G.; Sebestyén, Endre; Bernardis, Isabella; Eyras, Eduardo; Valcárcel, Juan (2013-12-12). “RBM5, 6, and 10 differentially regulate NUMB alternative splicing to control cancer cell proliferation”. Molecular Cell 52 (5): 720–733. doi:10.1016/j.molcel.2013.11.010. ISSN 1097-4164. PMID 24332178.
- ^ a b Inoue, Akira; Yamamoto, Naoki; Kimura, Masatsugu; Nishio, Koji; Yamane, Hideo; Nakajima, Koichi (2014-03-18). “RBM10 regulates alternative splicing”. FEBS letters 588 (6): 942–947. doi:10.1016/j.febslet.2014.01.052. ISSN 1873-3468. PMID 24530524.
- ^ Yang, Xinping; Coulombe-Huntington, Jasmin; Kang, Shuli; Sheynkman, Gloria M.; Hao, Tong; Richardson, Aaron; Sun, Song; Yang, Fan et al. (2016-02-11). “Widespread Expansion of Protein Interaction Capabilities by Alternative Splicing”. Cell 164 (4): 805–817. doi:10.1016/j.cell.2016.01.029. ISSN 1097-4172. PMC 4882190. PMID 26871637.
- ^ Sutherland, Leslie C.; Thibault, Philippe; Durand, Mathieu; Lapointe, Elvy; Knee, Jose M.; Beauvais, Ariane; Kalatskaya, Irina; Hunt, Sarah C. et al. (07 20, 2017). “Splicing arrays reveal novel RBM10 targets, including SMN2 pre-mRNA”. BMC molecular biology 18 (1): 19. doi:10.1186/s12867-017-0096-x. ISSN 1471-2199. PMC 5520337. PMID 28728573.
- ^ a b c d Sun, Yue; Bao, Yufang; Han, Wenjian; Song, Fan; Shen, Xianfeng; Zhao, Jiawei; Zuo, Ji; Saffen, David et al. (2017-08-21). “Autoregulation of RBM10 and cross-regulation of RBM10/RBM5 via alternative splicing-coupled nonsense-mediated decay”. Nucleic Acids Research 45 (14): 8524–8540. doi:10.1093/nar/gkx508. ISSN 1362-4962. PMC 5737846. PMID 28586478.
- ^ Collins, Katherine M.; Kainov, Yaroslav A.; Christodolou, Evangelos; Ray, Debashish; Morris, Quaid; Hughes, Timothy; Taylor, Ian A.; Makeyev, Eugene V. et al. (2017-06-20). “An RRM-ZnF RNA recognition module targets RBM10 to exonic sequences to promote exon exclusion”. Nucleic Acids Research 45 (11): 6761–6774. doi:10.1093/nar/gkx225. ISSN 1362-4962. PMC 5499739. PMID 28379442.
- ^ a b c Loiselle, Julie J.; Roy, Justin G.; Sutherland, Leslie C. (2017). “RBM10 promotes transformation-associated processes in small cell lung cancer and is directly regulated by RBM5”. PloS One 12 (6): e0180258. doi:10.1371/journal.pone.0180258. ISSN 1932-6203. PMC 5491171. PMID 28662214.
- ^ a b c Johnston, Jennifer J.; Teer, Jamie K.; Cherukuri, Praveen F.; Hansen, Nancy F.; Loftus, Stacie K.; NIH Intramural Sequencing Center (NISC); Chong, Karen; Mullikin, James C. et al. (2010-05-14). “Massively parallel sequencing of exons on the X chromosome identifies RBM10 as the gene that causes a syndromic form of cleft palate”. American Journal of Human Genetics 86 (5): 743–748. doi:10.1016/j.ajhg.2010.04.007. ISSN 1537-6605. PMC 2868995. PMID 20451169.
- ^ a b Gorlin, R. J.; Cervenka, J.; Anderson, R. C.; Sauk, J. J.; Bevis, W. D. (1970-02). “Robin's syndrome. A probably X-linked recessive subvariety exhibiting persistence of left superior vena cava and atrial septal defect”. American Journal of Diseases of Children (1960) 119 (2): 176–178. ISSN 0002-922X. PMID 5410571.
- ^ a b Imielinski, Marcin; Berger, Alice H.; Hammerman, Peter S.; Hernandez, Bryan; Pugh, Trevor J.; Hodis, Eran; Cho, Jeonghee; Suh, James et al. (2012-09-14). “Mapping the hallmarks of lung adenocarcinoma with massively parallel sequencing”. Cell 150 (6): 1107–1120. doi:10.1016/j.cell.2012.08.029. ISSN 1097-4172. PMC 3557932. PMID 22980975.
- ^ a b Seiler, Michael; Peng, Shouyong; Agrawal, Anant A.; Palacino, James; Teng, Teng; Zhu, Ping; Smith, Peter G.; Cancer Genome Atlas Research Network et al. (04 03, 2018). “Somatic Mutational Landscape of Splicing Factor Genes and Their Functional Consequences across 33 Cancer Types”. Cell Reports 23 (1): 282–296.e4. doi:10.1016/j.celrep.2018.01.088. ISSN 2211-1247. PMC 5933844. PMID 29617667.
- ^ a b Cieply, Benjamin; Carstens, Russ P. (2015-05). “Functional roles of alternative splicing factors in human disease”. Wiley interdisciplinary reviews. RNA 6 (3): 311–326. doi:10.1002/wrna.1276. ISSN 1757-7012. PMC 4671264. PMID 25630614.
- ^ a b Coomer, Alice O.; Black, Fiona; Greystoke, Alastair; Munkley, Jennifer; Elliott, David J. (2019-11). “Alternative splicing in lung cancer”. Biochimica Et Biophysica Acta. Gene Regulatory Mechanisms 1862 (11-12): 194388. doi:10.1016/j.bbagrm.2019.05.006. ISSN 1876-4320. PMID 31152916.
- ^ a b Rodor, Julie; FitzPatrick, David R.; Eyras, Eduardo; Cáceres, Javier F. (01 02, 2017). “The RNA-binding landscape of RBM10 and its role in alternative splicing regulation in models of mouse early development”. RNA biology 14 (1): 45–57. doi:10.1080/15476286.2016.1247148. ISSN 1555-8584. PMC 5270529. PMID 27763814.
- ^ “RBM10 RNA binding motif protein 10 [Homo sapiens (human) - Gene - NCBI]”. www.ncbi.nlm.nih.gov. 2020年12月5日閲覧。
- ^ a b c d e Inoue, Akira; Tsugawa, Katsuji; Tokunaga, Kazuaki; Takahashi, Kenichi P.; Uni, Shigehiko; Kimura, Masatsugu; Nishio, Koji; Yamamoto, Naoki et al. (2008-09). “S1-1 nuclear domains: characterization and dynamics as a function of transcriptional activity”. Biology of the Cell 100 (9): 523–535. doi:10.1042/BC20070142. ISSN 1768-322X. PMID 18315527.
- ^ a b Zheng, Sika; Damoiseaux, Robert; Chen, Liang; Black, Douglas L. (2013-06). “A broadly applicable high-throughput screening strategy identifies new regulators of Dlg4 (Psd-95) alternative splicing”. Genome Research 23 (6): 998–1007. doi:10.1101/gr.147546.112. ISSN 1549-5469. PMC 3668367. PMID 23636947.
- ^ Lim, Janghoo; Hao, Tong; Shaw, Chad; Patel, Akash J.; Szabó, Gábor; Rual, Jean-François; Fisk, C. Joseph; Li, Ning et al. (2006-05-19). “A protein-protein interaction network for human inherited ataxias and disorders of Purkinje cell degeneration”. Cell 125 (4): 801–814. doi:10.1016/j.cell.2006.03.032. ISSN 0092-8674. PMID 16713569.
- ^ Mohan, Nimmy; Kumar, Vikas; Kandala, Divya T.; Kartha, Chandrasekharan C.; Laishram, Rakesh S. (09 25, 2018). “A Splicing-Independent Function of RBM10 Controls Specific 3' UTR Processing to Regulate Cardiac Hypertrophy”. Cell Reports 24 (13): 3539–3553. doi:10.1016/j.celrep.2018.08.077. ISSN 2211-1247. PMID 30257214.
- ^ a b c Mueller, Cornelius F. H.; Berger, Anja; Zimmer, Sebastian; Tiyerili, Vedat; Nickenig, Georg (2009-08-01). “The heterogenous nuclear riboprotein S1-1 regulates AT1 receptor gene expression via transcriptional and posttranscriptional mechanisms”. Archives of Biochemistry and Biophysics 488 (1): 76–82. doi:10.1016/j.abb.2009.06.002. ISSN 1096-0384. PMID 19508861.
- ^ Treiber, Thomas; Treiber, Nora; Plessmann, Uwe; Harlander, Simone; Daiß, Julia-Lisa; Eichner, Norbert; Lehmann, Gerhard; Schall, Kevin et al. (2017-04-20). “A Compendium of RNA-Binding Proteins that Regulate MicroRNA Biogenesis”. Molecular Cell 66 (2): 270–284.e13. doi:10.1016/j.molcel.2017.03.014. ISSN 1097-4164. PMID 28431233.
- ^ a b c Jung, Ji Hoon; Lee, Hyemin; Cao, Bo; Liao, Peng; Zeng, Shelya X.; Lu, Hua (01 2020). “RNA-binding motif protein 10 induces apoptosis and suppresses proliferation by activating p53”. Oncogene 39 (5): 1031–1040. doi:10.1038/s41388-019-1034-9. ISSN 1476-5594. PMC 6994357. PMID 31591476.
- ^ Guan, Guofang; Li, Ranwei; Tang, Wenfang; Liu, Tiecheng; Su, Zhenzhong; Wang, Yan; Tan, Jingjin; Jiang, Shan et al. (2017-03). “Expression of RNA-binding motif 10 is associated with advanced tumor stage and malignant behaviors of lung adenocarcinoma cancer cells”. Tumour Biology: The Journal of the International Society for Oncodevelopmental Biology and Medicine 39 (3): 1010428317691740. doi:10.1177/1010428317691740. ISSN 1423-0380. PMID 28347232.
- ^ Kunimoto, Hiroyuki; Inoue, Akira; Kojima, Hirotada; Yang, Junhao; Zhao, Hong; Tsuruta, Daisuke; Nakajima, Koichi (2020-02). “RBM10 regulates centriole duplication in HepG2 cells by ectopically assembling PLK4-STIL complexes in the nucleus”. Genes to Cells: Devoted to Molecular & Cellular Mechanisms 25 (2): 100–110. doi:10.1111/gtc.12741. ISSN 1365-2443. PMID 31820547.
- ^ Pozzi, Berta; Bragado, Laureano; Mammi, Pablo; Torti, María Florencia; Gaioli, Nicolás; Gebhard, Leopoldo G.; García Solá, Martín E.; Vaz-Drago, Rita et al. (07 09, 2020). “Dengue virus targets RBM10 deregulating host cell splicing and innate immune response”. Nucleic Acids Research 48 (12): 6824–6838. doi:10.1093/nar/gkaa340. ISSN 1362-4962. PMC 7337517. PMID 32432721.
- ^ Salichs, Eulàlia; Ledda, Alice; Mularoni, Loris; Albà, M. Mar; de la Luna, Susana (2009-03). “Genome-wide analysis of histidine repeats reveals their role in the localization of human proteins to the nuclear speckles compartment”. PLoS genetics 5 (3): e1000397. doi:10.1371/journal.pgen.1000397. ISSN 1553-7404. PMC 2644819. PMID 19266028.
- ^ Goto, Yuji; Kimura, Hiroshi (2009-12). “Inactive X chromosome-specific histone H3 modifications and CpG hypomethylation flank a chromatin boundary between an X-inactivated and an escape gene”. Nucleic Acids Research 37 (22): 7416–7428. doi:10.1093/nar/gkp860. ISSN 0305-1048. PMC 2794193. PMID 19843608.
- ^ Stes, Elisabeth; Laga, Mathias; Walton, Alan; Samyn, Noortje; Timmerman, Evy; De Smet, Ive; Goormachtig, Sofie; Gevaert, Kris (2014-06-06). “A COFRADIC protocol to study protein ubiquitination”. Journal of Proteome Research 13 (6): 3107–3113. doi:10.1021/pr4012443. ISSN 1535-3907. PMID 24816145.
- ^ Akimov, Vyacheslav; Barrio-Hernandez, Inigo; Hansen, Sten V. F.; Hallenborg, Philip; Pedersen, Anna-Kathrine; Bekker-Jensen, Dorte B.; Puglia, Michele; Christensen, Stine D. K. et al. (07 2018). “UbiSite approach for comprehensive mapping of lysine and N-terminal ubiquitination sites”. Nature Structural & Molecular Biology 25 (7): 631–640. doi:10.1038/s41594-018-0084-y. ISSN 1545-9985. PMID 29967540.
- ^ Choudhary, Chunaram; Kumar, Chanchal; Gnad, Florian; Nielsen, Michael L.; Rehman, Michael; Walther, Tobias C.; Olsen, Jesper V.; Mann, Matthias (2009-08-14). “Lysine acetylation targets protein complexes and co-regulates major cellular functions”. Science (New York, N.Y.) 325 (5942): 834–840. doi:10.1126/science.1175371. ISSN 1095-9203. PMID 19608861.
- ^ Guo, Ailan; Gu, Hongbo; Zhou, Jing; Mulhern, Daniel; Wang, Yi; Lee, Kimberly A.; Yang, Vicky; Aguiar, Mike et al. (2014-01). “Immunoaffinity enrichment and mass spectrometry analysis of protein methylation”. Molecular & cellular proteomics: MCP 13 (1): 372–387. doi:10.1074/mcp.O113.027870. ISSN 1535-9484. PMC 3879628. PMID 24129315.
- ^ Cancer Genome Atlas Research Network (2014-07-31). “Comprehensive molecular profiling of lung adenocarcinoma”. Nature 511 (7511): 543–550. doi:10.1038/nature13385. ISSN 1476-4687. PMC 4231481. PMID 25079552.
- ^ Yuan, Yuan; Liu, Lingxiang; Chen, Hu; Wang, Yumeng; Xu, Yanxun; Mao, Huzhang; Li, Jun; Mills, Gordon B. et al. (05 09, 2016). “Comprehensive Characterization of Molecular Differences in Cancer between Male and Female Patients”. Cancer Cell 29 (5): 711–722. doi:10.1016/j.ccell.2016.04.001. ISSN 1878-3686. PMC 4864951. PMID 27165743.
- ^ Yin, Lin-Lin; Wen, Xin-Mian; Li, Ming; Xu, Yan-Mei; Zhao, Xiao-Feng; Li, Jing; Wang, Xiu-Wen (2018-11). “A gene mutation in RNA-binding protein 10 is associated with lung adenocarcinoma progression and poor prognosis”. Oncology Letters 16 (5): 6283–6292. doi:10.3892/ol.2018.9496. ISSN 1792-1074. PMC 6202477. PMID 30405763.
- ^ Powis, Zöe; Hart, Alexa; Cherny, Sara; Petrik, Igor; Palmaer, Erika; Tang, Sha; Jones, Carolyn (06 02, 2017). “Clinical diagnostic exome evaluation for an infant with a lethal disorder: genetic diagnosis of TARP syndrome and expansion of the phenotype in a patient with a newly reported RBM10 alteration”. BMC medical genetics 18 (1): 60. doi:10.1186/s12881-017-0426-3. ISSN 1471-2350. PMC 5455125. PMID 28577551.
- ^ Gripp, Karen W.; Hopkins, Elizabeth; Johnston, Jennifer J.; Krause, Caitlin; Dobyns, William B.; Biesecker, Leslie G. (2011-10). “Long-term survival in TARP syndrome and confirmation of RBM10 as the disease-causing gene”. American Journal of Medical Genetics. Part A 155A (10): 2516–2520. doi:10.1002/ajmg.a.34190. ISSN 1552-4833. PMC 3183328. PMID 21910224.
- ^ Niceta, Marcello; Barresi, Sabina; Pantaleoni, Francesca; Capolino, Rossella; Dentici, Maria Lisa; Ciolfi, Andrea; Pizzi, Simone; Bartuli, Andrea et al. (2019-06). “TARP syndrome: Long-term survival, anatomic patterns of congenital heart defects, differential diagnosis and pathogenetic considerations”. European Journal of Medical Genetics 62 (6): 103534. doi:10.1016/j.ejmg.2018.09.001. ISSN 1878-0849. PMID 30189253.
- ^ Højland, Allan T.; Lolas, Ihab; Okkels, Henrik; Lautrup, Charlotte K.; Diness, Birgitte R.; Petersen, Michael B.; Nielsen, Irene K. (12 2018). “First reported adult patient with TARP syndrome: A case report”. American Journal of Medical Genetics. Part A 176 (12): 2915–2918. doi:10.1002/ajmg.a.40638. ISSN 1552-4833. PMC 6587983. PMID 30462380.
- ^ Xia, Qiu-Yuan; Wang, Xiao-Tong; Zhan, Xue-Mei; Tan, Xiao; Chen, Hao; Liu, Yi; Shi, Shan-Shan; Wang, Xuan et al. (2017-05). “Xp11 Translocation Renal Cell Carcinomas (RCCs) With RBM10-TFE3 Gene Fusion Demonstrating Melanotic Features and Overlapping Morphology With t(6;11) RCC: Interest and Diagnostic Pitfall in Detecting a Paracentric Inversion of TFE3”. The American Journal of Surgical Pathology 41 (5): 663–676. doi:10.1097/PAS.0000000000000837. ISSN 1532-0979. PMID 28288037.
- ^ Argani, Pedram; Zhang, Lei; Reuter, Victor E.; Tickoo, Satish K.; Antonescu, Cristina R. (2017-05). “RBM10-TFE3 Renal Cell Carcinoma: A Potential Diagnostic Pitfall Due to Cryptic Intrachromosomal Xp11.2 Inversion Resulting in False-negative TFE3 FISH”. The American Journal of Surgical Pathology 41 (5): 655–662. doi:10.1097/PAS.0000000000000835. ISSN 1532-0979. PMC 5391276. PMID 28296677.
- ^ Kato, Ikuma; Furuya, Mitsuko; Baba, Masaya; Kameda, Yoichi; Yasuda, Masanori; Nishimoto, Koshiro; Oyama, Masafumi; Yamasaki, Toshinari et al. (2019-08). “RBM10-TFE3 renal cell carcinoma characterised by paracentric inversion with consistent closely split signals in break-apart fluorescence in-situ hybridisation: study of 10 cases and a literature review”. Histopathology 75 (2): 254–265. doi:10.1111/his.13866. ISSN 1365-2559. PMID 30908700.
- ^ a b Witkiewicz, Agnieszka K.; McMillan, Elizabeth A.; Balaji, Uthra; Baek, GuemHee; Lin, Wan-Chi; Mansour, John; Mollaee, Mehri; Wagner, Kay-Uwe et al. (2015-04-09). “Whole-exome sequencing of pancreatic cancer defines genetic diversity and therapeutic targets”. Nature Communications 6: 6744. doi:10.1038/ncomms7744. ISSN 2041-1723. PMC 4403382. PMID 25855536.
- ^ Furukawa, Toru; Kuboki, Yuko; Tanji, Etsuko; Yoshida, Shoko; Hatori, Takashi; Yamamoto, Masakazu; Shibata, Noriyuki; Shimizu, Kyoko et al. (2011). “Whole-exome sequencing uncovers frequent GNAS mutations in intraductal papillary mucinous neoplasms of the pancreas”. Scientific Reports 1: 161. doi:10.1038/srep00161. ISSN 2045-2322. PMC 3240977. PMID 22355676.
- ^ Giannakis, Marios; Mu, Xinmeng Jasmine; Shukla, Sachet A.; Qian, Zhi Rong; Cohen, Ofir; Nishihara, Reiko; Bahl, Samira; Cao, Yin et al. (2016-04-26). “Genomic Correlates of Immune-Cell Infiltrates in Colorectal Carcinoma”. Cell Reports 15 (4): 857–865. doi:10.1016/j.celrep.2016.03.075. ISSN 2211-1247. PMC 4850357. PMID 27149842.
- ^ Lawrence, Michael S.; Stojanov, Petar; Mermel, Craig H.; Robinson, James T.; Garraway, Levi A.; Golub, Todd R.; Meyerson, Matthew; Gabriel, Stacey B. et al. (2014-01-23). “Discovery and saturation analysis of cancer genes across 21 tumour types”. Nature 505 (7484): 495–501. doi:10.1038/nature12912. ISSN 1476-4687. PMC 4048962. PMID 24390350.
- ^ Ibrahimpasic, Tihana; Xu, Bin; Landa, Iñigo; Dogan, Snjezana; Middha, Sumit; Seshan, Venkatraman; Deraje, Shyam; Carlson, Diane L. et al. (2017-10-01). “Genomic Alterations in Fatal Forms of Non-Anaplastic Thyroid Cancer: Identification of MED12 and RBM10 as Novel Thyroid Cancer Genes Associated with Tumor Virulence”. Clinical Cancer Research: An Official Journal of the American Association for Cancer Research 23 (19): 5970–5980. doi:10.1158/1078-0432.CCR-17-1183. ISSN 1078-0432. PMC 5626586. PMID 28634282.
- ^ Antonello, Zeus A.; Hsu, Nancy; Bhasin, Manoj; Roti, Giovanni; Joshi, Mukta; Van Hummelen, Paul; Ye, Emily; Lo, Agnes S. et al. (2017-10-17). “Vemurafenib-resistance via de novo RBM genes mutations and chromosome 5 aberrations is overcome by combined therapy with palbociclib in thyroid carcinoma with BRAFV600E”. Oncotarget 8 (49): 84743–84760. doi:10.18632/oncotarget.21262. ISSN 1949-2553. PMC 5689570. PMID 29156680.
- ^ Ibrahimpasic, Tihana; Ghossein, Ronald; Shah, Jatin P.; Ganly, Ian (03 2019). “Poorly Differentiated Carcinoma of the Thyroid Gland: Current Status and Future Prospects”. Thyroid: Official Journal of the American Thyroid Association 29 (3): 311–321. doi:10.1089/thy.2018.0509. ISSN 1557-9077. PMC 6437626. PMID 30747050.
- ^ a b Kan, Zhengyan; Jaiswal, Bijay S.; Stinson, Jeremy; Janakiraman, Vasantharajan; Bhatt, Deepali; Stern, Howard M.; Yue, Peng; Haverty, Peter M. et al. (2010-08-12). “Diverse somatic mutation patterns and pathway alterations in human cancers”. Nature 466 (7308): 869–873. doi:10.1038/nature09208. ISSN 1476-4687. PMID 20668451.
- ^ Tian, Weijun; Hu, Weiyu; Shi, Xiaoling; Liu, Peng; Ma, Xiang; Zhao, Wei; Qu, Linlin; Zhang, Shuirong et al. (2020-04). “Comprehensive genomic profile of cholangiocarcinomas in China”. Oncology Letters 19 (4): 3101–3110. doi:10.3892/ol.2020.11429. ISSN 1792-1074. PMC 7074170. PMID 32256810.
- ^ Schwab, Marisa E.; Song, Hanbing; Mattis, Aras; Phelps, Andrew; Vu, Lan T.; Huang, Franklin W.; Nijagal, Amar (2020-03-24). “De novo somatic mutations and KRAS amplification are associated with cholangiocarcinoma in a patient with a history of choledochal cyst”. Journal of Pediatric Surgery. doi:10.1016/j.jpedsurg.2020.03.008. ISSN 1531-5037. PMID 32295706.
- ^ Juratli, Tareq A.; McCabe, Devin; Nayyar, Naema; Williams, Erik A.; Silverman, Ian M.; Tummala, Shilpa S.; Fink, Alexandria L.; Baig, Aymen et al. (11 2018). “DMD genomic deletions characterize a subset of progressive/higher-grade meningiomas with poor outcome”. Acta Neuropathologica 136 (5): 779–792. doi:10.1007/s00401-018-1899-7. ISSN 1432-0533. PMID 30123936.
- ^ Majd, Nazanin K.; Metrus, Nicolas R.; Santos-Pinheiro, Fernando; Trevino, Christopher R.; Fuller, Gregory N.; Huse, Jason T.; Chung, Caroline; Ketonen, Leena et al. (02 2019). “RBM10 truncation in astroblastoma in a patient with history of mandibular ameloblastoma: A case report”. Cancer Genetics 231-232: 41–45. doi:10.1016/j.cancergen.2019.01.001. ISSN 2210-7762. PMID 30803556.
- ^ Loiselle, Julie J.; Sutherland, Leslie C. (05 2018). “RBM10: Harmful or helpful-many factors to consider”. Journal of Cellular Biochemistry 119 (5): 3809–3818. doi:10.1002/jcb.26644. ISSN 1097-4644. PMC 5901003. PMID 29274279.
- ^ Misquitta-Ali, Christine M.; Cheng, Edith; O'Hanlon, Dave; Liu, Ni; McGlade, C. Jane; Tsao, Ming Sound; Blencowe, Benjamin J. (2011-01). “Global profiling and molecular characterization of alternative splicing events misregulated in lung cancer”. Molecular and Cellular Biology 31 (1): 138–150. doi:10.1128/MCB.00709-10. ISSN 1098-5549. PMC 3019846. PMID 21041478.
- ^ a b Hernández, Jordi; Bechara, Elias; Schlesinger, Doerte; Delgado, Javier; Serrano, Luis; Valcárcel, Juan (2016). “Tumor suppressor properties of the splicing regulatory factor RBM10”. RNA biology 13 (4): 466–472. doi:10.1080/15476286.2016.1144004. ISSN 1555-8584. PMC 4841610. PMID 26853560.
- ^ a b c Majd, Nazanin K.; Metrus, Nicolas R.; Santos-Pinheiro, Fernando; Trevino, Christopher R.; Fuller, Gregory N.; Huse, Jason T.; Chung, Caroline; Ketonen, Leena et al. (02 2019). “RBM10 truncation in astroblastoma in a patient with history of mandibular ameloblastoma: A case report”. Cancer Genetics 231-232: 41–45. doi:10.1016/j.cancergen.2019.01.001. ISSN 2210-7762. PMID 30803556.
- ^ a b Han, Li-Ping; Wang, Cun-Ping; Han, Si-Lin (2018-10). “Overexpression of RBM10 induces osteosarcoma cell apoptosis and inhibits cell proliferation and migration”. Medecine Sciences: M/S 34 Focus issue F1: 81–86. doi:10.1051/medsci/201834f114. ISSN 1958-5381. PMID 30403180.
- ^ Jin, Xin; Di, Xin; Wang, Ruimin; Ma, He; Tian, Chang; Zhao, Min; Cong, Shan; Liu, Jiaying et al. (06 2019). “RBM10 inhibits cell proliferation of lung adenocarcinoma via RAP1/AKT/CREB signalling pathway”. Journal of Cellular and Molecular Medicine 23 (6): 3897–3904. doi:10.1111/jcmm.14263. ISSN 1582-4934. PMC 6533519. PMID 30955253.
- ^ Sutherland, Leslie C.; Rintala-Maki, Nina D.; White, Ryan D.; Morin, Cory D. (2005-01-01). “RNA binding motif (RBM) proteins: a novel family of apoptosis modulators?”. Journal of Cellular Biochemistry 94 (1): 5–24. doi:10.1002/jcb.20204. ISSN 0730-2312. PMID 15514923.
- ^ Wang, Ke; Bacon, Mackensey L.; Tessier, Julie J.; Rintala-Maki, Nina D.; Tang, Vanessa; Sutherland, Leslie C. (2012). “RBM10 Modulates Apoptosis and Influences TNF-α Gene Expression”. Journal of Cell Death 5: 1–19. doi:10.4137/JCD.S9073. ISSN 1179-0660. PMC 4583097. PMID 26446321.
- ^ Sun, Xiuna; Jia, Mengqi; Sun, Wei; Feng, Lu; Gu, Chundong; Wu, Taihua (2019-02). “Functional role of RBM10 in lung adenocarcinoma proliferation”. International Journal of Oncology 54 (2): 467–478. doi:10.3892/ijo.2018.4643. ISSN 1791-2423. PMC 6317669. PMID 30483773.
- ^ Balachandran, Vinod P.; Łuksza, Marta; Zhao, Julia N.; Makarov, Vladimir; Moral, John Alec; Remark, Romain; Herbst, Brian; Askan, Gokce et al. (11 23, 2017). “Identification of unique neoantigen qualities in long-term survivors of pancreatic cancer”. Nature 551 (7681): 512–516. doi:10.1038/nature24462. ISSN 1476-4687. PMC 6145146. PMID 29132146.
- ^ Siegel, Rebecca L.; Miller, Kimberly D.; Jemal, Ahmedin (01 2018). “Cancer statistics, 2018”. CA: a cancer journal for clinicians 68 (1): 7–30. doi:10.3322/caac.21442. ISSN 1542-4863. PMID 29313949.
- ^ Mourtada-Maarabouni, Mirna; Williams, Gwyn T. (2002-07-04). “RBM5/LUCA-15--tumour suppression by control of apoptosis and the cell cycle?”. TheScientificWorldJournal 2: 1885–1890. doi:10.1100/tsw.2002.859. ISSN 1537-744X. PMC 6009235. PMID 12920317.
- ^ Oh, Juliana J.; Razfar, Ali; Delgado, Idolina; Reed, Rebecca A.; Malkina, Anna; Boctor, Baher; Slamon, Dennis J. (2006-04-01). “3p21.3 tumor suppressor gene H37/Luca15/RBM5 inhibits growth of human lung cancer cells through cell cycle arrest and apoptosis”. Cancer Research 66 (7): 3419–3427. doi:10.1158/0008-5472.CAN-05-1667. ISSN 0008-5472. PMID 16585163.
- ^ Fushimi, Kazuo; Ray, Payal; Kar, Amar; Wang, Lei; Sutherland, Leslie C.; Wu, Jane Y. (2008-10-14). “Up-regulation of the proapoptotic caspase 2 splicing isoform by a candidate tumor suppressor, RBM5”. Proceedings of the National Academy of Sciences of the United States of America 105 (41): 15708–15713. doi:10.1073/pnas.0805569105. ISSN 1091-6490. PMC 2572934. PMID 18840686.
- ^ Bonnal, Sophie; Martínez, Concepción; Förch, Patrik; Bachi, Angela; Wilm, Matthias; Valcárcel, Juan (2008-10-10). “RBM5/Luca-15/H37 regulates Fas alternative splice site pairing after exon definition”. Molecular Cell 32 (1): 81–95. doi:10.1016/j.molcel.2008.08.008. ISSN 1097-4164. PMID 18851835.
- ^ Sutherland, Leslie C.; Wang, Ke; Robinson, Andrew G. (2010-03). “RBM5 as a putative tumor suppressor gene for lung cancer”. Journal of Thoracic Oncology: Official Publication of the International Association for the Study of Lung Cancer 5 (3): 294–298. doi:10.1097/JTO.0b013e3181c6e330. ISSN 1556-1380. PMID 20186023.
- ^ Jamsai, Duangporn; Watkins, D. Neil; O'Connor, Anne E.; Merriner, D. Jo; Gursoy, Selen; Bird, Anthony D.; Kumar, Beena; Miller, Alistair et al. (11 24, 2017). “In vivo evidence that RBM5 is a tumour suppressor in the lung”. Scientific Reports 7 (1): 16323. doi:10.1038/s41598-017-15874-9. ISSN 2045-2322. PMC 5701194. PMID 29176597.
- ^ Wang, Qiwei; Wang, Fang; Zhong, Waisheng; Ling, Hang; Wang, Jixuan; Cui, Jie; Xie, Tao; Wen, Senli et al. (2019-05-20). “RNA-binding protein RBM6 as a tumor suppressor gene represses the growth and progression in laryngocarcinoma”. Gene 697: 26–34. doi:10.1016/j.gene.2019.02.025. ISSN 1879-0038. PMID 30772516.
- ^ Deckert, Jochen; Hartmuth, Klaus; Boehringer, Daniel; Behzadnia, Nastaran; Will, Cindy L.; Kastner, Berthold; Stark, Holger; Urlaub, Henning et al. (2006-07). “Protein composition and electron microscopy structure of affinity-purified human spliceosomal B complexes isolated under physiological conditions”. Molecular and Cellular Biology 26 (14): 5528–5543. doi:10.1128/MCB.00582-06. ISSN 0270-7306. PMC 1592722. PMID 16809785.
- ^ Papasaikas, Panagiotis; Tejedor, J. Ramón; Vigevani, Luisa; Valcárcel, Juan (2015-01-08). “Functional splicing network reveals extensive regulatory potential of the core spliceosomal machinery”. Molecular Cell 57 (1): 7–22. doi:10.1016/j.molcel.2014.10.030. ISSN 1097-4164. PMID 25482510.
- ^ Ule, Jernej; Blencowe, Benjamin J. (10 17, 2019). “Alternative Splicing Regulatory Networks: Functions, Mechanisms, and Evolution”. Molecular Cell 76 (2): 329–345. doi:10.1016/j.molcel.2019.09.017. ISSN 1097-4164. PMID 31626751.
関連文献
[編集]- “Oligo-capping: a simple method to replace the cap structure of eukaryotic mRNAs with oligoribonucleotides”. Gene 138 (1–2): 171–4. (January 1994). doi:10.1016/0378-1119(94)90802-8. PMID 8125298.
- “Construction and characterization of a full length-enriched and a 5'-end-enriched cDNA library”. Gene 200 (1–2): 149–56. (October 1997). doi:10.1016/S0378-1119(97)00411-3. PMID 9373149.
- “DNA cloning using in vitro site-specific recombination”. Genome Research 10 (11): 1788–95. (November 2000). doi:10.1101/gr.143000. PMC 310948. PMID 11076863.
- “Toward a catalog of human genes and proteins: sequencing and analysis of 500 novel complete protein coding human cDNAs”. Genome Research 11 (3): 422–35. (March 2001). doi:10.1101/gr.GR1547R. PMC 311072. PMID 11230166.
- “Regulation of alternative splicing by SRrp86 and its interacting proteins”. Molecular and Cellular Biology 23 (21): 7437–47. (November 2003). doi:10.1128/MCB.23.21.7437-7447.2003. PMC 207616. PMID 14559993.
- “Large-scale characterization of HeLa cell nuclear phosphoproteins”. Proceedings of the National Academy of Sciences of the United States of America 101 (33): 12130–5. (August 2004). Bibcode: 2004PNAS..10112130B. doi:10.1073/pnas.0404720101. PMC 514446. PMID 15302935.
- “Phosphoproteomic analysis of the developing mouse brain”. Molecular & Cellular Proteomics 3 (11): 1093–101. (November 2004). doi:10.1074/mcp.M400085-MCP200. PMID 15345747.
- “From ORFeome to biology: a functional genomics pipeline”. Genome Research 14 (10B): 2136–44. (October 2004). doi:10.1101/gr.2576704. PMC 528930. PMID 15489336.
- “Towards a proteome-scale map of the human protein-protein interaction network”. Nature 437 (7062): 1173–8. (October 2005). Bibcode: 2005Natur.437.1173R. doi:10.1038/nature04209. PMID 16189514.
- “The LIFEdb database in 2006”. Nucleic Acids Research 34 (Database issue): D415-8. (January 2006). doi:10.1093/nar/gkj139. PMC 1347501. PMID 16381901.
- “Positive correlation between the expression of X-chromosome RBM genes (RBMX, RBM3, RBM10) and the proapoptotic Bax gene in human breast cancer”. Journal of Cellular Biochemistry 97 (6): 1275–82. (April 2006). doi:10.1002/jcb.20725. PMID 16552754.
- “Global, in vivo, and site-specific phosphorylation dynamics in signaling networks”. Cell 127 (3): 635–48. (November 2006). doi:10.1016/j.cell.2006.09.026. PMID 17081983.